
Размер генома — это общее количество ДНК , содержащееся в одной копии одного полного генома . Обычно ее измеряют в единицах массы в пикограммах (триллионные доли (10-12 ) грамма , сокращенно пг) или, реже, в дальтонах , или как общее количество пар нуклеотидных оснований , обычно в мегаоснованиях (миллионы пар оснований, сокращенно Мб или Мбит/с). Один пикограмм равен 978 мегабазам. [1] В диплоидных организмах размер генома часто используется как синоним термина C-значение .
Сложность организма не прямо пропорциональна размеру его генома; общее содержание ДНК широко варьируется между биологическими таксонами. Некоторые одноклеточные организмы имеют гораздо больше ДНК, чем люди, по причинам, которые остаются неясными (см. « Загадка некодирующей ДНК и значения C »).

Термин «размер генома» часто ошибочно приписывают статье Ральфа Хинегарднера 1976 года [2] даже в дискуссиях, посвященных конкретно терминологии в этой области исследований (например, Greilhuber 2005 [3] ). Примечательно, что Хинегарднер [2] использовал этот термин только один раз: в названии. На самом деле этот термин, похоже, впервые появился в 1968 году, когда Хинегарднер в последнем абзаце другой статьи задался вопросом, действительно ли «содержание клеточной ДНК отражает размер генома». [4] В этом контексте «размер генома» использовался в смысле генотипа , обозначающего количество генов .
В статье, представленной всего два месяца спустя, Wolf et al. (1969) [5] использовали термин «размер генома» повсюду и в его нынешнем использовании; поэтому этим авторам, вероятно, следует приписать создание этого термина в его современном смысле. К началу 1970-х годов «размер генома» стал широко использоваться в его нынешнем определении, вероятно, в результате его включения во влиятельную книгу Сусуму Оно «Эволюция путем дупликации генов» , опубликованную в 1970 году. [6]
С появлением различных молекулярных методов за последние 50 лет были проанализированы размеры геномов тысяч эукариот , и эти данные доступны в онлайн-базах данных для животных, растений и грибов (см. Внешние ссылки). Размер ядерного генома обычно измеряется у эукариот с использованием либо денситометрических измерений ядер, окрашенных по Фельгену (ранее с использованием специализированных денситометров, теперь чаще с использованием компьютерного анализа изображений [7] ) или проточной цитометрии . У прокариот преобладающими методами определения размера генома являются гель-электрофорез в импульсном поле и полное секвенирование генома .
Хорошо известно, что размеры ядерного генома сильно различаются у разных видов эукариот. У животных они варьируются более чем в 3300 раз, а у наземных растений — примерно в 1000 раз. [8] [9] Сообщалось, что геномы протистов различаются по размеру более чем в 300 000 раз, но верхний предел этого диапазона ( Амеба ) был поставлен под сомнение. [ кем? ] У эукариот (но не прокариотов) размер генома не пропорционален числу генов , присутствующих в нем, - наблюдение, которое считалось совершенно нелогичным до открытия некодирующей ДНК и которое стало известно как « C- Ценностный парадокс » в результате. Однако, хотя в несоответствии между размером генома и числом генов больше нет никакого парадоксального аспекта, этот термин продолжает широко использоваться. В целях концептуального разъяснения один автор предположил, что различные загадки, которые остаются в отношении изменения размера генома, вместо этого более точно представляют собой головоломку или загадку (так называемую « загадку C-значения »).
Размер генома коррелирует с рядом измеримых характеристик на уровне клеток и организмов, включая размер клеток, скорость деления клеток и, в зависимости от таксона , размер тела, скорость метаболизма , скорость развития, сложность органов , географическое распространение или риск исчезновения . [8] [9] На основе доступных в настоящее время данных о полностью секвенированном геноме (по состоянию на апрель 2009 г.), число логарифмически преобразованных генов образует линейную корреляцию с логарифмическим размером генома у бактерий, архей, вирусов и органелл вместе взятых, тогда как нелинейная корреляция (полунатуральный логарифм) корреляция наблюдается у эукариот. [10] Хотя последнее противоречит предыдущему мнению о том, что для эукариот корреляции не существует, наблюдаемая нелинейная корреляция для эукариот может отражать непропорционально быстрое увеличение некодирующей ДНК во все более крупных эукариотических геномах. Хотя данные секвенирования генома практически смещены в сторону небольших геномов, что может поставить под угрозу точность эмпирически полученной корреляции, а окончательное доказательство корреляции еще предстоит получить путем секвенирования некоторых из крупнейших эукариотических геномов, текущие данные, похоже, не исключают возможная корреляция.

У человека общий женский диплоидный ядерный геном на клетку простирается на 6,37 пар гигабаз (Гбп), имеет длину 208,23 см и вес 6,51 пикограмма (пг). [11] Мужские значения: 6,27 Гб, 205,00 см, 6,41 стр. [11] Каждый полимер ДНК может содержать сотни миллионов нуклеотидов, например, в хромосоме 1 . Хромосома 1 — самая крупная хромосома человека, содержащая примерно 220 миллионов пар оснований .Длина 85 мм в выпрямленном состоянии. [12]
У эукариот , помимо ядерной ДНК , имеется еще митохондриальная ДНК (мтДНК), которая кодирует определенные белки, используемые митохондриями. МтДНК обычно относительно мала по сравнению с ядерной ДНК. Например, митохондриальная ДНК человека образует замкнутые кольцевые молекулы, каждая из которых содержит 16 569 [13] [14] пар оснований ДНК, [15] причем каждая такая молекула в норме содержит полный набор митохондриальных генов. Каждая митохондрия человека содержит в среднем около 5 таких молекул мтДНК. [15] Каждая человеческая клетка содержит около 100 митохондрий, что дает общее количество молекул мтДНК на человеческую клетку около 500. [15] Однако количество митохондрий на клетку также варьируется в зависимости от типа клетки, и яйцеклетка может содержать 100 000 митохондрий. , что соответствует до 1 500 000 копий митохондриального генома (составляющего до 90% ДНК клетки). [16]
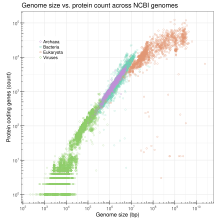
Редукция генома , также известная как деградация генома , — это процесс, при котором геном организма сжимается по сравнению с геномом его предков. Размер геномов регулярно колеблется, и уменьшение размера генома наиболее существенно у бактерий .
Наиболее эволюционно значимые случаи редукции генома можно наблюдать в эукариотических органеллах, которые, как известно, произошли от бактерий: митохондриях и пластидах . Эти органеллы произошли от первичных эндосимбионтов , которые были способны выживать внутри клетки-хозяина и которые также были необходимы клетке-хозяину для выживания. Многие современные митохондрии содержат менее 20 генов во всем геноме, тогда как современная свободноживущая бактерия обычно имеет не менее 1000 генов. Многие гены, по-видимому, были перенесены в ядро хозяина , тогда как другие просто были потеряны, а их функции заменены отростками хозяина.
Другие бактерии стали эндосимбионтами или облигатными внутриклеточными патогенами и в результате испытали обширную редукцию генома. В этом процессе, по-видимому, доминирует генетический дрейф , возникающий из-за небольшого размера популяции , низкой скорости рекомбинации и высокой скорости мутаций , в отличие от отбора меньших геномов. [ нужна цитата ] Некоторые свободноживущие морские бактериопланктоны также демонстрируют признаки редукции генома, которые, как предполагается, вызваны естественным отбором. [17] [18] [19]
Облигатные эндосимбиотические виды характеризуются полной неспособностью выживать вне среды обитания . Эти виды стали серьезной угрозой для здоровья человека, поскольку они часто способны уклоняться от иммунной системы человека и манипулировать средой обитания для получения питательных веществ. Распространенным объяснением этих манипулятивных способностей является их неизменно компактная и эффективная геномная структура. Эти небольшие геномы являются результатом массовой потери чужеродной ДНК, явления, которое связано исключительно с потерей свободноживущей стадии. До 90% генетического материала может быть потеряно при эволюционном переходе вида от свободноживущего к облигатному внутриклеточному образу жизни. Во время этого процесса будущий паразит подвергается воздействию среды, богатой метаболитами, где ему каким-то образом необходимо спрятаться внутри клетки-хозяина, эти факторы уменьшают сохранение и увеличивают генетический дрейф, что приводит к ускорению потери несущественных генов. [20] [21] [22] Распространенные примеры видов с уменьшенным геномом включают Buchnera aphidicola , Rickettsia prowazekii и Mycobacterium leprae . Один облигатный эндосимбионт цикадок , Nasuia deltocephalinicola , имеет самый маленький геном, известный в настоящее время среди клеточных организмов, размером 112 т.п.н. [23] Несмотря на патогенность большинства эндосимбионтов, некоторые облигатные внутриклеточные виды оказывают положительное влияние на приспособленность своих хозяев.
Модель редуктивной эволюции была предложена как попытка определить геномные сходства, наблюдаемые у всех облигатных эндосимбионтов. [24] Эта модель иллюстрирует четыре общие особенности редуцированных геномов и облигатных внутриклеточных видов:
Основываясь на этой модели, становится ясно, что эндосимбионты сталкиваются с другими адаптивными проблемами, чем свободноживущие виды, и, как показал анализ между различными паразитами, их наборы генов чрезвычайно различаются, что приводит нас к выводу, что миниатюризация генома происходит по другой схеме. для разных симбионтов. [26] [27] [28]
или просто:
В 1991 году Джон В. Дрейк предложил общее правило: частота мутаций внутри генома и его размер обратно коррелируют. [29] Было обнаружено, что это правило приблизительно верно для простых геномов, таких как геномы ДНК-вирусов и одноклеточных организмов. Его основа неизвестна.
Было высказано предположение, что небольшой размер РНК-вирусов обусловлен трехчастной зависимостью между точностью репликации, размером генома и генетической сложностью. Большинству РНК-вирусов не хватает средства проверки РНК, что ограничивает точность их репликации и, следовательно, размер их генома. Это также было описано как «парадокс Эйгена». [30] Исключение из правила небольших размеров генома у РНК-вирусов обнаружено у нидовирусов . Эти вирусы, по-видимому, приобрели экзорибонуклеазу 3'-5' (ExoN), что позволило увеличить размер генома. [31]
В 1972 году Майкл Дэвид Беннетт [32] выдвинул гипотезу о наличии корреляции с содержанием ДНК и объемом ядра, в то время как Коммонер , а до него Вант-Хофф и Воробей постулировали, что даже размер клетки и продолжительность клеточного цикла контролируются количеством ДНК. . [33] [34] Более поздние теории привели нас к обсуждению возможности существования механизма, который физически ограничивает развитие генома до оптимального размера. [35]
Эти объяснения были оспорены в статье Кавальер-Смита [36] , где автор указал, что способ понять связь между размером генома и объемом клетки связан с теорией скелета. Ядро этой теории связано с объемом клетки, определяемым адаптационным балансом между преимуществами и недостатками большего размера клеток, оптимизацией соотношения ядро:цитоплазма (кариоплазматическое соотношение) [37] [38] и концепцией того, что более крупные геномы обеспечивает более склонность к накоплению дупликативных транспозонов как следствие более высокого содержания некодирующей скелетной ДНК. [36] Кавальер-Смит также предположил, что в результате редукции клеток ядро будет более склонно к отбору в пользу делеции по сравнению с дупликацией. [36]
С экономической точки зрения, поскольку фосфора и энергии не хватает, уменьшение количества ДНК всегда должно быть в центре внимания эволюции, если только не будет получена польза. Тогда случайное удаление будет в основном вредным и невыбранным из-за снижения достигнутой приспособленности, но иногда исключение также будет полезным. Этот компромисс между экономией и накоплением некодирующей ДНК является ключом к поддержанию кариоплазматического соотношения.
Основной вопрос, лежащий в основе процесса миниатюризации генома, заключается в том, происходит ли он крупными шагами или вследствие постоянной эрозии содержания генов. Чтобы оценить эволюцию этого процесса, необходимо сравнить геном предка с тем, где предположительно произошло сокращение. Благодаря сходству генного состава Buchnera aphidicola и кишечных бактерий Escherichia coli идентичность 89% для 16S рДНК и 62% для ортологичных генов позволила пролить свет на механизм миниатюризации генома. [39] Геном эндосимбионта B. aphidicola характеризуется размером генома, который в семь раз меньше генома E. coli (643 кб по сравнению с 4,6 Мб) [40] [41] и может рассматриваться как подмножество кишечного генома. генный инвентарь бактерий. [41] В результате конфронтации двух геномов выяснилось, что некоторые гены сохраняются как частично деградированные. [41], что указывает на то, что функция была потеряна во время процесса и что последующие события эрозии сократили длину, как это зарегистрировано у Rickettsia . [42] [43] [44] Эта гипотеза подтверждается анализом псевдогенов Бюхнера , где количество делеций было более чем в десять раз выше по сравнению с инсерцией. [44]
У Rickettsia prowazekii , как и у других бактерий с малым геномом, этот мутуалистический эндосимбионт испытал значительное снижение функциональной активности с серьезным исключением по сравнению с другими паразитами, которые все еще сохраняют биосинтетическую способность производить аминокислоты, необходимые его хозяину. [45] [46] [41] Общими эффектами сокращения генома этого эндосимбионта и других паразитов являются снижение способности вырабатывать фосфолипиды, репарацию и рекомбинацию, а также общее преобразование состава гена в более богатый АТ. [47] содержание из-за мутаций и замен. [20] [45] Доказательством удаления функции репарации и рекомбинации является потеря гена Rec A, гена, участвующего в пути рекомбиназы . Это событие произошло при удалении более крупного участка, содержащего десять генов, общим размером почти 10 т.п.н. [41] [45] То же самое произошло с uvr A, uvr B и uvr C, генами, кодирующими эксцизионные ферменты, участвующие в восстановлении поврежденной ДНК из-за воздействия ультрафиолета. [39]
Одним из наиболее вероятных механизмов объяснения сокращения генома является хромосомная перестройка, поскольку вставку/делецию большей части последовательности легче обнаружить во время гомологичной рекомбинации по сравнению с нелегитимной, поэтому распространение мобильных элементов будет положительно влияют на скорость удаления. [36] Потеря этих генов на ранних стадиях миниатюризации не только выполняет эту функцию, но и должна играть роль в эволюции последующих делеций. Доказательства того, что более крупное событие удаления произошло до того, как меньшая делеция, возникли в результате сравнения генома Бакнеры и реконструированного предка, где утраченные гены на самом деле не разбросаны случайным образом в гене предка, а агрегированы, и существует отрицательная связь. между количеством потерянных генов и длиной спейсеров. [39] Событие небольших локальных инделей играет незначительную роль в редукции генома [48], особенно на ранних стадиях, когда большее количество генов становится излишним. [49] [39]
Вместо этого произошли отдельные события из-за отсутствия давления отбора для сохранения генов, особенно если часть пути потеряла свою функцию во время предыдущей делеции. Примером этого является удаление Rec F, гена, необходимого для функции Rec A, и его фланкирующих генов. [50] Одно из последствий удаления такого количества последовательностей затронуло даже регуляцию остальных генов. Потеря большой части генома фактически может привести к потере промоторных последовательностей. Фактически это может подтолкнуть отбор для эволюции полицистронных областей с положительным эффектом как на уменьшение размера [51], так и на эффективность транскрипции. [52]
Один из примеров миниатюризации генома произошел с микроспоридиями , анаэробным внутриклеточным паразитом членистоногих, развившимся из аэробных грибов.
В ходе этого процесса митосомы [53] формировались в результате превращения митохондрий в реликт, лишенный геномов и метаболической активности, за исключением производства железо-серных центров и способности проникать в клетки-хозяева. [54] [55] За исключением рибосом , также миниатюризированных, многие другие органеллы были почти утрачены в процессе формирования самого маленького генома, обнаруженного у эукариот. [36] По сравнению со своим возможным предком, зигомикотиновыми грибами, микроспоридии сократили свой геном, уничтожив почти 1000 генов и сократив даже размер белков и генов, кодирующих белки. [56] Этот экстремальный процесс стал возможен благодаря выгодному отбору клеток меньшего размера, вызванному паразитизмом.
Другой пример миниатюризации представлен наличием нуклеоморфов , порабощенных ядер, внутри клетки двух разных водорослей, криптофитов и хлорарахней . [57]
Нуклеоморфы характеризуются одним из самых маленьких известных геномов (551 и 380 т.п.н.), и, как было замечено для микроспоридий, некоторые геномы заметно уменьшены в длине по сравнению с другими эукариотами из-за фактического отсутствия некодирующей ДНК. [36] Самый интересный фактор представляет собой сосуществование этих маленьких ядер внутри клетки, которая содержит другое ядро, которое никогда не подвергалось такой редукции генома. Более того, даже если клетки-хозяева имеют разные объемы от вида к виду и, как следствие, изменчивость размера генома, нуклеоморф остается инвариантным, что означает двойной эффект отбора внутри одной и той же клетки.
{{cite book}}: |work=игнорируется ( помощь )