PubMed — это бесплатная поисковая система , обеспечивающая доступ в первую очередь к базе данных справок и рефератов MEDLINE по наукам о жизни и биомедицинским темам. Национальная медицинская библиотека США (NLM) при Национальных институтах здравоохранения поддерживает базу данных как часть системы поиска информации Entrez . [1]
С 1971 по 1997 год онлайн-доступ к базе данных MEDLINE осуществлялся в основном через институциональные учреждения, такие как университетские библиотеки . [2] PubMed, впервые выпущенный в январе 1996 года, открыл эру частного, бесплатного поиска в MEDLINE дома и в офисе. [3] Система PubMed предлагалась бесплатно публике начиная с июня 1997 года. [2]
Помимо MEDLINE, PubMed предоставляет доступ к:
Многие записи PubMed содержат ссылки на полные тексты статей, некоторые из которых находятся в свободном доступе, часто в PubMed Central [5] и на местных зеркалах, таких как Europe PubMed Central . [6]
Информацию о журналах, индексируемых в MEDLINE и доступных через PubMed, можно найти в каталоге NLM. [7]
По состоянию на 23 мая 2023 года [обновлять]в PubMed имеется более 35 миллионов цитат и рефератов, относящихся к 1966 году, выборочно к 1865 году и очень выборочно к 1809 году. По состоянию на ту же дату [обновлять]24,6 миллиона записей PubMed перечислены вместе с их рефератами, и 26,8 млн записей имеют ссылки на полнотекстовые версии (из них 10,9 млн статей доступны в полнотекстовом режиме бесплатно). [8] За последние 10 лет (до 31 декабря 2019 г.) ежегодно добавлялось в среднем около миллиона новых записей.
В 2016 году NLM изменила систему индексирования, чтобы издатели могли напрямую исправлять опечатки и ошибки в статьях, проиндексированных PubMed. [9]
Сообщается, что в PubMed включены некоторые статьи, опубликованные в хищнических журналах. Политика MEDLINE и PubMed по выбору журналов для включения в базу данных немного различается. Слабость критериев и процедур индексации журналов в PubMed Central может привести к утечке публикаций из журналов-хищников в PubMed. [10] Национальная медицинская библиотека ответила, что отдельные журнальные статьи могут быть включены в PMC для поддержки политики публичного доступа спонсоров исследований и что строгая политика в отношении журналов и издателей обеспечивает целостность литературных баз данных NLM. [11]
Новый интерфейс PubMed был запущен в октябре 2009 года и поощрял использование таких быстрых поисковых формул, как у Google; их также называют поиском «телеграмм». [12] По умолчанию результаты сортируются по «Самым последним», но это можно изменить на «Лучшее совпадение», «Дата публикации», «Первый автор», «Последний автор», «Журнал» или «Название». [13]
Дизайн и домен веб-сайта PubMed были обновлены в январе 2020 года и стали стандартными 15 мая 2020 года с обновленными и новыми функциями. [14] Многие исследователи, часто пользующиеся сайтом, отреагировали критично. [15]
Доступ к PubMed/MEDLINE можно получить через портативные устройства, используя, например, опцию «PICO» (для целенаправленных клинических вопросов), созданную NLM. [16] Также доступна опция «PubMed Mobile», обеспечивающая доступ к упрощенной версии PubMed для мобильных устройств. [17]
Простой поиск в PubMed можно выполнить, введя ключевые аспекты предмета в окно поиска PubMed.
PubMed переводит эту первоначальную формулировку поиска и автоматически добавляет имена полей, соответствующие термины MeSH (медицинские предметные рубрики), синонимы, логические операторы и соответствующим образом «вкладывает» полученные термины, значительно улучшая формулировку поиска, в частности, путем регулярного комбинирования (с использованием оператора OR). оператор) текстовые слова и термины MeSH. [ нужна цитата ]
Примеры, приведенные в руководстве PubMed [18], демонстрируют, как работает этот автоматический процесс:
Причины Лунатизм переводится как («этиология» [Подзаголовок] ИЛИ «этиология» [Все поля] ИЛИ «причины» [Все поля] ИЛИ «причинность» [Термины MeSH] ИЛИ «причинность» [Все поля]) И ( « сомнамбулизм «[Термины MeSH] ИЛИ «сомнамбулизм» [Все поля] ИЛИ («сон» [Все поля] И «ходьба» [Все поля]) ИЛИ «ходьба во сне» [Все поля])
Так же,
Soft Attack Aspirin Prevention переводится как («инфаркт миокарда» [Термины MeSH] ИЛИ («миокард» [Все поля] И «инфаркт» [Все поля]) ИЛИ «инфаркт миокарда» [Все поля] ИЛИ («сердце» [Все поля]) Поля] И «атака» [Все поля]) ИЛИ «сердечный приступ» [Все поля]) И («аспирин» [Термины MeSH] ИЛИ «аспирин» [Все поля]) И («профилактика и контроль» [Подзаголовок] ИЛИ («профилактика»[Все поля] И «контроль»[Все поля]) ИЛИ «профилактика и контроль»[Все поля] ИЛИ «профилактика»[Все поля])
Для оптимального поиска в PubMed необходимо понимать его основной компонент, MEDLINE, и особенно словарь, контролируемый MeSH (медицинские предметные рубрики), используемый для индексирования статей MEDLINE. Они также могут требовать сложных стратегий поиска, использования имен полей (тегов), правильного использования ограничений и других функций; Справочные библиотекари и специалисты по поиску предлагают услуги по поиску. [19] [20]
Поиск в окне поиска PubMed рекомендуется только для поиска однозначных тем или новых вмешательств, для которых еще не создан заголовок MeSH, а также для поиска коммерческих марок лекарств и имен собственных. Это также полезно, когда нет подходящего заголовка или дескриптор представляет собой частичный аспект. Поиск с использованием тезауруса MeSH более точен и дает меньше нерелевантных результатов. Кроме того, это избавляет от недостатка свободного текстового поиска, при котором необходимо учитывать различия в написании, единственном/множественном числе или сокращении. С другой стороны, статьи, недавно включенные в базу данных, которым еще не присвоены дескрипторы, не будут найдены. Поэтому, чтобы гарантировать исчерпывающий поиск, необходимо использовать комбинацию контролируемых языковых заголовков и свободных текстовых терминов. [21]
Когда журнальная статья индексируется, многочисленные параметры статьи извлекаются и сохраняются в виде структурированной информации. К таким параметрам относятся: тип статьи (термины MeSH, например, «Клиническое исследование»), вторичные идентификаторы (термины MeSH), язык, страна журнала или история публикации (дата электронной публикации, дата публикации в печатном журнале).
Параметр «Тип публикации» позволяет осуществлять поиск по типу публикации , включая отчеты о различных видах клинических исследований. [22]
С июля 2005 года процесс индексирования статей MEDLINE извлекает идентификаторы из аннотации статьи и помещает их в поле под названием «Вторичный идентификатор» (SI). Поле вторичного идентификатора предназначено для хранения номеров доступа к различным базам данных данных о молекулярных последовательностях, экспрессии генов или химических соединениях, а также идентификаторов клинических испытаний. Для клинических испытаний PubMed извлекает идентификаторы исследований для двух крупнейших реестров исследований: ClinicalTrials.gov (идентификатор NCT) и Международного стандартного реестра номеров рандомизированных контролируемых исследований (идентификатор IRCTN). [23]
Ссылка, которая считается особенно актуальной, может быть отмечена и обозначена «похожие статьи». При необходимости можно выбрать несколько исследований и создать соответствующие статьи для всех из них (в PubMed или любой другой базе данных NCBI Entrez), используя опцию «Найти связанные данные». Связанные статьи затем перечисляются в порядке «связанности». Чтобы создать эти списки связанных статей, PubMed сравнивает слова из заголовка и аннотации каждой цитаты, а также присвоенные заголовки MeSH, используя мощный алгоритм взвешивания слов. [24] Функция «похожие статьи» была признана настолько точной, что авторы статьи предложили использовать ее вместо полного поиска. [25]
PubMed автоматически ссылается на термины и подзаголовки MeSH. Примеры: «неприятный запах изо рта» связан с «неприятным запахом изо рта» (и включается в поиск), «сердечный приступ» с «инфарктом миокарда», «рак молочной железы» с «новообразованиями молочной железы». При необходимости эти термины MeSH автоматически «расширяются», то есть включают более конкретные термины. Такие термины, как «уход за больными», автоматически связываются с «уход [MeSH]» или «уход [подзаголовок]». Эта функция называется автоматическим сопоставлением терминов и по умолчанию применяется при свободном текстовом поиске, но не при точном поиске фраз (т. е. заключении поискового запроса в двойные кавычки). [26] Эта функция делает поиск в PubMed более чувствительным и позволяет избежать ложноотрицательных (пропущенных) совпадений за счет компенсации разнообразия медицинской терминологии. [26]
PubMed не применяет автоматическое сопоставление термина в следующих случаях: при написании цитируемой фразы (например, «аллотрансплантат почки»), при усечении звездочкой (например, аллотрансплантат почки*) и при просмотре с метками полей (например, Рак [ти]). [21]
Дополнительный сервис PubMed «Мой NCBI» (с бесплатной регистрацией) предоставляет инструменты для
и широкий спектр других опций. [27] Доступ к разделу «Мой NCBI» возможен с любого компьютера, имеющего веб-доступ. Более ранняя версия «My NCBI» называлась «PubMed Cubby». [28]
LinkOut — это средство NLM, позволяющее связать и сделать доступными полнотекстовые фонды местных журналов. [29] Около 3200 центров (в основном академических учреждений) участвуют в этом средстве NLM (по состоянию на март 2010 г. [обновлять]), от Ольборгского университета в Дании до ZymoGenetics в Сиэтле. [30] Пользователи этих учреждений видят логотип своего учреждения в результатах поиска PubMed (если журнал ведется в этом учреждении) и могут получить доступ к полному тексту. Link Out объединяется с Outside Tool после основного обновления платформы, которое выйдет летом 2019 года. [31]
В 2016 году PubMed позволяет авторам статей комментировать статьи, индексируемые PubMed. Первоначально эта функция тестировалась в пилотном режиме (с 2013 года) и стала постоянной в 2016 году. [32] В феврале 2018 года работа PubMed Commons была прекращена в связи с тем, что «использование осталось минимальным». [33] [34]
AskMEDLINE, инструмент запросов на естественном языке с произвольным текстом для MEDLINE/PubMed, разработанный NLM, также подходит для портативных устройств. [35]
PMID (идентификатор PubMed или уникальный идентификатор PubMed) [ 36] представляет собой уникальное целочисленное значение , начинающееся с 1, присвоенное каждой записи PubMed. PMID — это не то же самое, что PMCID (идентификатор PubMed Central), который является идентификатором всех работ, опубликованных в PubMed Central с бесплатным доступом . [37]
Присвоение публикации PMID или PMCID ничего не говорит читателю о типе или качестве контента. PMID присваиваются письмам редактору , редакционным мнениям, колонкам с комментариями и любым другим материалам, которые редактор решает включить в журнал, а также рецензируемым статьям. Наличие идентификационного номера также не является доказательством того, что документы не были отозваны из-за мошенничества, некомпетентности или неправомерных действий. Объявлению о любых исправлениях в оригинальных статьях может быть присвоен PMID.
Каждое число, введенное в окно поиска PubMed, по умолчанию рассматривается как PMID. Таким образом, любую ссылку в PubMed можно найти с помощью PMID.
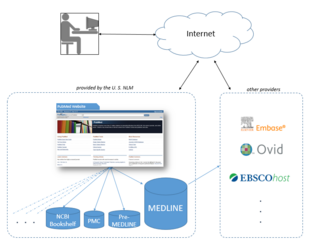
Национальная медицинская библиотека сдает в аренду информацию MEDLINE ряду частных поставщиков, таких как Embase , Ovid , Dialog , EBSCO , Knowledge Finder и многим другим коммерческим, некоммерческим и академическим поставщикам. [38] По состоянию на октябрь 2008 года [обновлять]было выдано более 500 лицензий, более 200 из них — поставщикам услуг за пределами США. Поскольку лицензии на использование данных MEDLINE доступны бесплатно, NLM фактически предоставляет бесплатную площадку для тестирования широкого спектра [39] альтернативных интерфейсов и сторонних дополнений к PubMed, одной из очень немногих крупных, профессионально курируемых баз данных, которые предлагают это. вариант.
Лу приводит образец из 28 текущих и бесплатных веб-версий PubMed, не требующих установки или регистрации, которые сгруппированы в четыре категории: [39]
Поскольку большинство этих и других альтернатив в основном полагаются на данные PubMed/MEDLINE, арендованные по лицензии у NLM/PubMed, был предложен термин «производные PubMed». [39] Без необходимости хранить около 90 ГБ исходных наборов данных PubMed любой может писать приложения PubMed, используя программный интерфейс eutils-application, как описано в книге Эрика Сэйерса «Подробно об электронных утилитах: параметры, синтаксис и многое другое». , Кандидат наук. [50] Различные генераторы формата цитирования, принимающие в качестве входных данных номера PMID, являются примерами веб-приложений, использующих программный интерфейс eutils-application. Примеры веб-страниц включают «Генератор цитирования – Мик Шредер», «Генератор цитирования в публикации» – «Ультразвук недели», PMID2cite и «Процитируйте это для меня».
Альтернативные методы анализа данных в PubMed используют такие среды программирования, как Matlab , Python или R. В этих случаях запросы PubMed записываются в виде строк кода и передаются в PubMed, а затем ответ обрабатывается непосредственно в среде программирования. Код можно автоматизировать для систематических запросов по различным ключевым словам, таким как болезнь, год, органы и т. д.
Помимо своей традиционной роли биомедицинской базы данных, PubMed стал распространенным ресурсом для обучения биомедицинских языковых моделей . [51] Последние достижения в этой области включают разработку таких моделей, как PubMedGPT, модель с параметрами 2,7B, обученную на данных PubMed Стэнфордским CRFM, и BiomedCLIP-PubMedBERT от Microsoft, которая использует пары рисунков и подписей из PubMed Central для обработки изображения и языка. Эти модели демонстрируют значительный потенциал данных PubMed в расширении возможностей искусственного интеллекта в медицинских исследованиях и приложениях здравоохранения. Такие достижения подчеркивают растущее пересечение крупномасштабного анализа данных и разработки искусственного интеллекта в биомедицинской области.
Данные, доступные PubMed, можно зеркалировать локально с помощью неофициального инструмента, такого как MEDOC. [52]
Миллионы записей PubMed дополняют различные наборы открытых данных об открытом доступе , такие как Unpaywall . Инструменты анализа данных, такие как Unpaywall Journals, используются библиотеками для помощи при отмене крупных сделок : библиотеки могут избежать подписки на материалы, которые уже предоставляются в мгновенном открытом доступе через открытые архивы, такие как PubMed Central. [53]