Интрон — это любая нуклеотидная последовательность внутри гена , которая не экспрессируется и не действует в конечном продукте РНК . Слово «интрон» происходит от термина «интрагенный регион » , то есть «участок внутри гена». [1] Термин «интрон» относится как к последовательности ДНК внутри гена, так и к соответствующей последовательности РНК в транскриптах РНК . [2] Неинтронные последовательности, которые соединяются в результате процессинга РНК с образованием зрелой РНК, называются экзонами . [3]
Интроны встречаются в генах большинства организмов и многих вирусов и могут располагаться как в генах, кодирующих белки, так и в генах, функционирующих как РНК (некодирующие гены). Существует четыре основных типа интронов: интроны тРНК, интроны группы I, интроны группы II и сплайсосомные интроны (см. ниже). Интроны редки у бактерий и архей (прокариотов), но большинство эукариотических генов содержат множество сплайсосомных интронов.
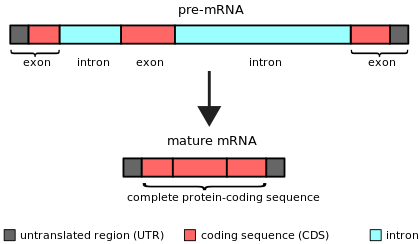
Интроны были впервые обнаружены в генах, кодирующих белки аденовируса , [4] [5] и впоследствии идентифицированы в генах, кодирующих гены транспортных РНК и рибосомальных РНК. Сейчас известно, что интроны встречаются в самых разных генах организмов, бактерий [6] и вирусов во всех биологических царствах.
Тот факт, что гены расщепляются или прерываются интронами, был независимо открыт в 1977 году Филипом Алленом Шарпом и Ричардом Дж. Робертсом , за что они разделили Нобелевскую премию по физиологии и медицине в 1993 году. [7] Термин «интрон» был введен американским биохимиком. Уолтер Гилберт : [1]
«Представление о цистроне [т.е. гене]... должно быть заменено понятием транскрипционной единицы, содержащей области, которые будут потеряны из зрелого мессенджера – которые я предлагаю называть интронами (для внутригенных областей) – чередующиеся с областями, которые будут выражены – экзоны». (Гилберт, 1978)
Термин «интрон» также относится к интрацистрону , т. е. дополнительной части ДНК, которая возникает внутри цистрона . [8]
Хотя интроны иногда называют промежуточными последовательностями , [9] термин «промежуточная последовательность» может относиться к любому из нескольких семейств внутренних последовательностей нуклеиновых кислот, которые не присутствуют в конечном продукте гена, включая интеины , нетранслируемые области (UTR) и нуклеотиды. удаляются путем редактирования РНК , помимо интронов.
Наблюдается, что частота интронов в разных геномах широко варьируется в зависимости от спектра биологических организмов. Например, интроны чрезвычайно распространены в ядерном геноме челюстных позвоночных (например, человека, мыши и рыбы-фугу (фугу)), где гены, кодирующие белки, почти всегда содержат несколько интронов, тогда как интроны редко встречаются в ядерных генах некоторых эукариотических микроорганизмов. , [10] например , пекарские/пивные дрожжи ( Saccharomyces cerevisiae ). Напротив, митохондриальные геномы позвоночных животных полностью лишены интронов, тогда как геномы эукариотических микроорганизмов могут содержать множество интронов. [11]
Особенно крайним случаем является ген dhc7 дрозофилы , содержащий интрон размером ≥3,6 мегабаз (Мб), для транскрипции которого требуется примерно три дня. [12] [13] С другой стороны, исследование 2015 года предполагает, что самая короткая известная длина интрона многоклеточных животных составляет 30 пар оснований (п.н.), принадлежащих человеческому гену MST1L . [14] Самые короткие известные интроны принадлежат гетеротрихным инфузориям, таким как Stentor coeruleus , у которых большинство (>95%) интронов имеют длину 15 или 16 п.н. [15]
Сплайсинг всех интронсодержащих молекул РНК внешне аналогичен описанному выше. Однако различные типы интронов были идентифицированы посредством изучения структуры интронов с помощью анализа последовательности ДНК, а также генетического и биохимического анализа реакций сплайсинга РНК. Были идентифицированы по крайней мере четыре различных класса интронов:
Предполагается, что интроны группы III относятся к пятому семейству, но мало что известно о биохимическом аппарате, который обеспечивает их сплайсинг. По-видимому, они связаны с интронами группы II и, возможно, с интронами сплайсосом. [16]
Интроны ядерной пре-мРНК (сплайсосомные интроны) характеризуются специфическими последовательностями интронов, расположенными на границах между интронами и экзонами. [17] Эти последовательности распознаются молекулами сплайсосомной РНК, когда инициируются реакции сплайсинга. [18] Кроме того, они содержат точку ветвления, определенную нуклеотидную последовательность вблизи 3'-конца интрона, которая ковалентно связывается с 5'-концом интрона во время процесса сплайсинга, образуя разветвленную ( лариат ) [ необходимы разъяснения] (сложный жаргон) ] интрон. Помимо этих трех коротких консервативных элементов, последовательности ядерных интронов пре-мРНК сильно варьируют. Интроны ядерной пре-мРНК часто намного длиннее окружающих их экзонов.
Интроны транспортной РНК, удаление которых зависит от белков, находятся в определенном месте внутри антикодоновой петли несплайсированных предшественников тРНК и удаляются эндонуклеазой сплайсинга тРНК. Затем экзоны соединяются вместе вторым белком — лигазой сплайсинга тРНК. [19] Обратите внимание, что самосплайсинговые интроны также иногда обнаруживаются в генах тРНК. [20]
Интроны группы I и группы II обнаружены в генах, кодирующих белки ( информационная РНК ), транспортную РНК и рибосомальную РНК у очень широкого круга живых организмов. [21] [22] После транскрипции в РНК интроны группы I и группы II также осуществляют обширные внутренние взаимодействия, которые позволяют им сворачиваться в специфическую, сложную трехмерную архитектуру . Эта сложная архитектура позволяет некоторым интронам группы I и группы II осуществлять самосплайсинг , то есть молекула РНК, содержащая интрон, может перестроить свою собственную ковалентную структуру так, чтобы точно удалить интрон и соединить экзоны вместе в правильном порядке. В некоторых случаях в сплайсинге участвуют определенные интрон-связывающие белки, действующие таким образом, что помогают интрону сворачиваться в трехмерную структуру, необходимую для активности самосплайсинга. Интроны группы I и группы II отличаются различным набором внутренних консервативных последовательностей и складчатых структур, а также тем, что при сплайсинге молекул РНК, содержащих интроны группы II, образуются разветвленные интроны (как и у сплайсосомных РНК), тогда как интроны группы I используют не -кодируемый гуанозиновый нуклеотид (обычно GTP) для инициации сплайсинга, добавляя его к 5'-концу вырезанного интрона.
Сплайсосома представляет собой очень сложную структуру, содержащую до ста белков и пять различных РНК. Субстратом реакции является длинная молекула РНК, а реакции переэтерификации, катализируемые сплайсосомой, требуют объединения сайтов, которые могут находиться на расстоянии тысяч нуклеотидов друг от друга. [23] [24] Все биохимические реакции связаны с известным уровнем ошибок, и чем сложнее реакция, тем выше уровень ошибок. Поэтому неудивительно, что реакция сплайсинга, катализируемая сплайсосомой, имеет значительную частоту ошибок, даже несмотря на то, что существуют дополнительные сплайсосомные факторы, которые подавляют случайное расщепление загадочных сайтов сплайсинга. [25]
В идеальных обстоятельствах реакция сплайсинга, вероятно, будет точной на 99,999% (коэффициент ошибок 10 -5 ), и правильные экзоны будут соединены, а правильный интрон будет удален. [26] Однако эти идеальные условия требуют очень близкого совпадения с лучшими последовательностями сайтов сплайсинга и отсутствия каких-либо конкурирующих последовательностей загадочных сайтов сплайсинга внутри интронов, и эти условия редко встречаются в крупных эукариотических генах, которые могут охватывать более 40 тысяч пар оснований. Недавние исследования показали, что фактическая частота ошибок может значительно превышать 10 -5 и достигать 2 или 3% ошибок (коэффициент ошибок 2 или 3 x 10 -2 ) на ген. [27] [28] [29] Дополнительные исследования показывают, что частота ошибок составляет не менее 0,1% на интрон. [30] [31] Этот относительно высокий уровень ошибок сплайсинга объясняет, почему большинство вариантов сплайсинга быстро разрушаются в результате бессмысленного распада. [32] [33]
Наличие неаккуратных сайтов связывания внутри генов приводит к ошибкам сплайсинга, и может показаться странным, что эти сайты не были устранены естественным отбором. Аргументы в пользу их устойчивости аналогичны аргументам в пользу мусорной ДНК. [30] [34]
Хотя мутации, которые создают или разрушают сайты связывания, могут быть слегка вредными, большое количество возможных таких мутаций делает неизбежным, что некоторые из них достигнут фиксации в популяции. Это особенно актуально для таких видов, как человек, с относительно небольшой эффективной численностью популяции в долгосрочной перспективе. Таким образом, вполне вероятно, что геном человека несет значительную нагрузку субоптимальных последовательностей, которые вызывают генерацию аберрантных изоформ транскриптов. В этом исследовании мы представляем прямые доказательства того, что это действительно так. [30]
Хотя каталитическая реакция может быть достаточно точной для эффективного процесса большую часть времени, общая частота ошибок может быть частично ограничена точностью транскрипции, поскольку ошибки транскрипции приводят к мутациям, которые создают загадочные сайты сплайсинга. Кроме того, частота ошибок транскрипции 10–5–10–6 настолько высока, что один из каждых 25 000 транскрибируемых экзонов будет иметь ошибку включения в один из сайтов сплайсинга, приводящую к пропущенному интрону или пропущенному экзону. Почти все мультиэкзонные гены будут производить неправильно сплайсированные транскрипты, но частота этого фонового шума будет зависеть от размера генов, количества интронов и качества последовательностей сайтов сплайсинга. [28] [31]
В некоторых случаях варианты сплайсинга будут возникать в результате мутаций в гене (ДНК). Это могут быть полиморфизмы SNP, которые создают загадочный сайт сплайсинга или мутируют функциональный сайт. Это также могут быть мутации соматических клеток, влияющие на сплайсинг конкретной ткани или клеточной линии. [35] [36] [37] Когда мутантный аллель находится в гетерозиготном состоянии, это приведет к образованию двух обильных сплайсинговых вариантов; один функциональный и один нефункциональный. В гомозиготном состоянии мутантные аллели могут вызывать генетическое заболевание, такое как гемофилия, обнаруженная у потомков королевы Виктории, когда мутация в одном из интронов гена фактора свертывания крови создает загадочный 3'-сайт сплайсинга, что приводит к аберрантному сплайсингу. [38] Значительная часть смертей людей от болезней может быть вызвана мутациями, которые мешают нормальному сплайсингу; в основном путем создания загадочных сайтов сплайсинга. [39] [36]
Неправильно сплайсированные транскрипты можно легко обнаружить, а их последовательности ввести в онлайн-базы данных. Их обычно описывают как транскрипты с «альтернативным сплайсингом», что может сбивать с толку, поскольку этот термин не делает различия между реальным, биологически значимым, альтернативным сплайсингом и шумом обработки, возникающим из-за ошибок сплайсинга. Одной из центральных проблем в области альтернативного сплайсинга является определение различий между этими двумя возможностями. Многие ученые утверждают, что нулевая гипотеза должна быть шумом сплайсинга, возлагая бремя доказательства на тех, кто утверждает, что альтернативный сплайсинг биологически значим. По мнению этих ученых, утверждение о функции должно сопровождаться убедительными доказательствами того, что несколько функциональных продуктов производятся одним и тем же геном. [40] [41]
Хотя интроны не кодируют белковые продукты, они являются неотъемлемой частью регуляции экспрессии генов. Некоторые интроны сами по себе кодируют функциональные РНК посредством дальнейшего процессинга после сплайсинга с образованием некодирующих молекул РНК . [42] Альтернативный сплайсинг широко используется для создания нескольких белков из одного гена. Более того, некоторые интроны играют важную роль в широком спектре регуляторных функций экспрессии генов, таких как нонсенс-опосредованный распад [43] и экспорт мРНК. [44]
После первоначального открытия интронов в генах, кодирующих белки эукариотического ядра, возникли серьезные споры о том, были ли интроны в современных организмах унаследованы от общего древнего предка (так называемая гипотеза ранних интронов) или же они появились в гены сравнительно недавно вступили в эволюционный процесс (так называемая гипотеза позднего появления интронов). Другая теория состоит в том, что сплайсосома и интрон-экзонная структура генов являются пережитком мира РНК (гипотеза «интроны прежде всего»). [45] До сих пор ведутся серьезные споры о том, какая из этих гипотез наиболее правильна, но на данный момент общепринято мнение, что после образования первой эукариотической клетки интроны группы II бактериального эндосимбионта вторглись в геном хозяина. Вначале эти самосплайсинговые интроны вырезали себя из предшественника мРНК, но со временем некоторые из них утратили эту способность, и их вырезанию в транс-трансформации пришлось способствовать с помощью других интронов группы II. Со временем появилось несколько специфических транс-действующих интронов, которые стали предшественниками мяРНК сплайсосомы . Эффективность сплайсинга повышалась за счет ассоциации со стабилизирующими белками с образованием примитивной сплайсосомы. [46] [47] [48] [49]
Ранние исследования последовательностей геномной ДНК широкого круга организмов показывают, что интрон-экзонная структура гомологичных генов у разных организмов может сильно различаться. [50] Более поздние исследования полных геномов эукариот показали, что длина и плотность (интроны/ген) интронов значительно различаются между родственными видами. Например, в то время как геном человека содержит в среднем 8,4 интрона на ген (139 418 в геноме), одноклеточный гриб Encephalitozoon cuniculi содержит только 0,0075 интронов на ген (15 интронов в геноме). [51] Поскольку эукариоты произошли от общего предка ( общее происхождение ), в ходе эволюции должно было произойти значительное увеличение или потеря интронов. [52] [53] Считается, что этот процесс является предметом отбора с тенденцией к увеличению интронов у более крупных видов из-за их меньшего размера популяции и наоборот у более мелких (особенно одноклеточных) видов. [54] Биологические факторы также влияют на то, какие гены в геноме теряют или накапливают интроны. [55] [56] [57]
Альтернативный сплайсинг экзонов внутри гена после удаления интрона приводит к большей вариабельности белковых последовательностей, транслируемых из одного гена, позволяя генерировать множество родственных белков из одного гена и одного транскрипта мРНК-предшественника. Контроль альтернативного сплайсинга РНК осуществляется сложной сетью сигнальных молекул, которые реагируют на широкий спектр внутриклеточных и внеклеточных сигналов.
Интроны содержат несколько коротких последовательностей, которые важны для эффективного сплайсинга, таких как акцепторные и донорные сайты на обоих концах интрона, а также сайт точки ветвления, которые необходимы для правильного сплайсинга сплайсосомой . Известно, что некоторые интроны усиливают экспрессию гена, в котором они содержатся, посредством процесса, известного как интрон-опосредованное усиление (IME).
Активно транскрибируемые участки ДНК часто образуют R-петли , уязвимые для повреждения ДНК . В генах дрожжей с высокой экспрессией интроны ингибируют образование R-петли и возникновение повреждений ДНК. [58] Полногеномный анализ как у дрожжей, так и у людей показал, что интрон-содержащие гены снижают уровни R-петли и уменьшают повреждение ДНК по сравнению с безинтронными генами с аналогичной экспрессией. [58] Вставка интрона в ген, склонный к R-петле, также может подавлять образование и рекомбинацию R-петли . Боннет и др. (2017) [58] предположили, что функция интронов по поддержанию генетической стабильности может объяснить их эволюционное сохранение в определенных местах, особенно в высокоэкспрессируемых генах.
Физическое присутствие интронов способствует клеточной устойчивости к голоданию за счет усиленной интронами репрессии генов рибосомальных белков путей восприятия питательных веществ. [59]
Интроны могут теряться или приобретаться в ходе эволюции, как показывают многие сравнительные исследования ортологичных генов. Последующие анализы выявили тысячи примеров событий потери и приобретения интронов, и было высказано предположение, что появление эукариотов или начальные стадии эволюции эукариот включало вторжение интронов. [60] Были идентифицированы и известны два окончательных механизма потери интронов: потеря интронов, опосредованная обратной транскриптазой (RTMIL) и геномные делеции. [61] Однако окончательные механизмы приобретения интронов остаются неуловимыми и противоречивыми. На данный момент известно как минимум семь механизмов усиления интронов: транспозиция интрона, вставка транспозона, тандемная геномная дупликация, перенос интрона, усиление интрона во время репарации двухцепочечного разрыва (DSBR), вставка интрона группы II и интронизация. Теоретически, происхождение недавно полученных интронов должно быть проще всего определить из-за отсутствия мутаций, вызванных хозяином, однако даже недавно полученные интроны не возникли ни в одном из вышеупомянутых механизмов. Эти результаты, таким образом, поднимают вопрос о том, не могут ли предложенные механизмы увеличения интронов описать механистическое происхождение многих новых интронов, потому что они не являются точными механизмами увеличения интронов, или же существуют другие, еще не открытые процессы, генерирующие новые интроны. интроны. [62]
При транспозиции интрона, наиболее часто предполагаемом механизме получения интрона, считается, что сплайсированный интрон осуществляет обратный сплайсинг либо в свою собственную мРНК, либо в другую мРНК в положении, в котором ранее не было интронов. Эта содержащая интрон мРНК затем подвергается обратной транскрипции, и полученная в результате интрон-содержащая кДНК может затем вызывать получение интрона посредством полной или частичной рекомбинации с его исходным геномным локусом. Вставки транспозонов также могут приводить к созданию интронов. Такая вставка могла бы интронизировать транспозон без нарушения кодирующей последовательности, когда транспозон вставляется в последовательность AGGT, что приводит к дупликации этой последовательности на каждой стороне транспозона. Пока не понятно, почему эти элементы сращиваются: случайно или в результате какого-то предпочтительного действия транспозона. При тандемной геномной дупликации из-за сходства консенсусных донорных и акцепторных сайтов сплайсинга, которые оба очень напоминают AGGT, тандемная геномная дупликация экзонного сегмента, содержащего последовательность AGGT, генерирует два потенциальных сайта сплайсинга. При распознавании сплайсосомой последовательность между исходным и дублированным AGGT будет сращена, что приведет к созданию интрона без изменения кодирующей последовательности гена. Репарация двухцепочечных разрывов посредством негомологичного соединения концов была недавно идентифицирована как источник прироста интронов, когда исследователи выявили короткие прямые повторы, фланкирующие 43% полученных интронов у дафний. [62] Однако для статистической значимости эти числа необходимо сравнить с количеством консервативных интронов, окруженных повторами в других организмах. Было высказано предположение, что для вставки интрона группы II ретрохоминг интрона группы II в ядерный ген вызывает недавнее увеличение сплайсосомного интрона.
Было высказано предположение, что перенос интрона приводит к увеличению интрона, когда паралог или псевдоген получает интрон, а затем переносит этот интрон посредством рекомбинации в место, где отсутствует интрон, в его сестринском паралоге. Интронизация — это процесс, посредством которого мутации создают новые интроны из ранее экзонной последовательности. Таким образом, в отличие от других предложенных механизмов усиления интронов, этот механизм не требует вставки или генерации ДНК для создания нового интрона. [62]
Единственный гипотетический механизм недавнего увеличения интронов, не имеющий каких-либо прямых доказательств, - это механизм вставки интронов группы II, который, продемонстрированный in vivo, отменяет экспрессию генов. [63] Таким образом, интроны группы II, вероятно, являются предполагаемыми предками сплайсосомных интронов, действуют как сайт-специфические ретроэлементы и больше не несут ответственности за прирост интронов. [64] [65] Тандемная геномная дупликация является единственным предложенным механизмом, подтверждающим экспериментальные данные in vivo: короткая внутригенная тандемная дупликация может вставлять новый интрон в ген, кодирующий белок, оставляя соответствующую пептидную последовательность неизменной. [66] Этот механизм также имеет обширные косвенные доказательства, подтверждающие идею о том, что тандемная геномная дупликация является распространенным механизмом получения интронов. Возможно тестирование других предложенных механизмов in vivo, в частности, получения интронов во время DSBR, переноса интронов и интронизации, хотя эти механизмы должны быть продемонстрированы in vivo, чтобы закрепить их как реальные механизмы получения интронов. Дальнейший геномный анализ, особенно на уровне популяции, может затем количественно оценить относительный вклад каждого механизма, возможно, выявляя видоспецифичные предубеждения, которые могут пролить свет на различные скорости увеличения интронов у разных видов. [62]
Состав:
Сращивание:
Функция
Другие: