
Метагеномика — это исследование генетического материала, полученного непосредственно из экологических или клинических образцов с помощью метода, называемого секвенированием . Эту широкую область можно также назвать геномикой окружающей среды , экогеномикой , геномикой сообщества или микробиомикой .
В то время как традиционная микробиология , секвенирование и геномика микробных геномов полагаются на культивируемые клональные культуры , раннее секвенирование генов окружающей среды клонировало определенные гены (часто ген 16S рРНК ) для создания профиля разнообразия в природном образце. Такая работа показала, что подавляющее большинство микробного биоразнообразия было упущено из-за методов культивирования. [2]
Благодаря своей способности раскрывать ранее скрытое разнообразие микроскопической жизни, метагеномика предлагает мощный способ понимания микробного мира, который может революционизировать понимание биологии. [3] Поскольку стоимость секвенирования ДНК продолжает падать, метагеномика теперь позволяет исследовать экологию микробов в гораздо большем масштабе и деталях, чем раньше. В недавних исследованиях используется либо « дробовик », либо ПЦР- направленное секвенирование, чтобы получить в значительной степени объективные образцы всех генов от всех членов отобранных сообществ. [4]
Термин «метагеномика» впервые был использован Джо Хандельсманом , Робертом М. Гудманом , Мишель Р. Рондон, Джоном Клэрди и Шоном Ф. Брэйди и впервые появился в публикации в 1998 году. [5] Термин «метагеном» отсылал к идее о том, что Коллекция генов, секвенированных из окружающей среды, может быть проанализирована аналогично изучению одного генома . В 2005 году Кевин Чен и Лиор Пахтер (исследователи из Калифорнийского университета в Беркли ) определили метагеномику как «применение современной техники геномики без необходимости изоляции и лабораторного культивирования отдельных видов». [6]
Традиционное секвенирование начинается с культивирования идентичных клеток в качестве источника ДНК . Однако ранние метагеномные исследования показали, что во многих средах, вероятно, существуют большие группы микроорганизмов, которые невозможно культивировать и , следовательно, невозможно секвенировать. Эти ранние исследования были сосредоточены на последовательностях 16S рибосомальной РНК (рРНК), которые относительно короткие, часто консервативны внутри одного вида и, как правило, различаются между видами. Было обнаружено множество последовательностей 16S рРНК , которые не принадлежат ни одному из известных культивируемых видов , что указывает на существование множества неизолированных организмов. Эти исследования генов рибосомальной РНК, взятых непосредственно из окружающей среды, показали, что методы, основанные на культивировании , обнаруживают в образце менее 1% видов бактерий и архей . [2] Большая часть интереса к метагеномике связана с этими открытиями, которые показали, что подавляющее большинство микроорганизмов ранее оставалось незамеченным.
В 1980-х годах первые молекулярные работы в этой области проводились Норманом Р. Пейсом и его коллегами, которые использовали ПЦР для изучения разнообразия последовательностей рибосомальных РНК. [7] Результаты этих революционных исследований побудили Пейса еще в 1985 году предложить идею клонирования ДНК непосредственно из образцов окружающей среды. [8] Это привело к первому отчету об выделении и клонировании массивной ДНК из образца окружающей среды, опубликованному Пейсом и его коллегами в 1991 году [9] , когда Пейс работал на факультете биологии в Университете Индианы . Значительные усилия гарантировали, что это не были ложноположительные результаты ПЦР , и подтвердили существование сложного сообщества неизученных видов. Хотя эта методология ограничивалась исследованием высококонсервативных, некодирующих белки генов , она подтвердила ранние наблюдения, основанные на морфологии микробов, о том, что разнообразие было гораздо более сложным, чем было известно методами культивирования. Вскоре после этого, в 1995 году, Хили сообщил о метагеномном выделении функциональных генов из «зообиблиотек», сконструированных из сложной культуры организмов окружающей среды, выращенных в лаборатории на сушеных травах . [10] Покинув лабораторию Пейса, Эдвард ДеЛонг продолжил работу в этой области и опубликовал работу, которая в значительной степени заложила основу для филогении окружающей среды, основанной на сигнатурных последовательностях 16S, начиная с создания его группой библиотек из морских образцов. [11]
В 2002 году Майя Брейтбарт , Форест Ровер и их коллеги использовали метод секвенирования окружающей среды (см. ниже), чтобы показать, что 200 литров морской воды содержат более 5000 различных вирусов. [12] Последующие исследования показали, что в стуле человека содержится более тысячи видов вирусов и, возможно, миллион различных вирусов на килограмм морских отложений , включая множество бактериофагов . По сути, все вирусы в этих исследованиях представляли собой новые виды. В 2004 году Джин Тайсон, Джилл Бэнфилд и их коллеги из Калифорнийского университета в Беркли и Объединенного института генома секвенировали ДНК, извлеченную из дренажной системы кислотной шахты . [13] В результате этих усилий были получены полные или почти полные геномы нескольких бактерий и архей , которые ранее сопротивлялись попыткам их культивирования. [14]
Начиная с 2003 года Крейг Вентер , руководитель параллельного проекта «Геном человека» , финансируемого из частных источников , возглавил Глобальную экспедицию по отбору проб океана (GOS), совершая кругосветное плавание и собирая метагеномные образцы на протяжении всего путешествия. Все эти образцы были секвенированы с использованием дробовика в надежде, что будут идентифицированы новые геномы (и, следовательно, новые организмы). Пилотный проект, проведенный в Саргассовом море , обнаружил ДНК почти 2000 различных видов , включая 148 типов бактерий , никогда ранее не встречавшихся. [15] Вентер тщательно исследовал западное побережье Соединенных Штатов и в 2006 году завершил двухлетнюю экспедицию по исследованию Балтийского , Средиземного и Черного морей . Анализ метагеномных данных, собранных во время этого путешествия, выявил две группы организмов: одна состоит из таксонов, адаптированных к условиям окружающей среды «пир или голод», а вторая состоит из относительно меньшего количества, но более обильных и широко распространенных таксонов, состоящих в основном из планктона . [16]
В 2005 году Стефан Шустер из Университета штата Пенсильвания и его коллеги опубликовали первые последовательности образца окружающей среды, полученные с помощью высокопроизводительного секвенирования , в данном случае массово-параллельного пиросеквенирования , разработанного 454 Life Sciences . [17] Еще одна ранняя статья в этой области появилась в 2006 году Робертом Эдвардсом, Форестом Роуэром и коллегами из Государственного университета Сан-Диего . [18]

Восстановление последовательностей ДНК длиной более нескольких тысяч пар оснований из образцов окружающей среды было очень трудным, пока недавние достижения в области молекулярно-биологических методов не позволили создать библиотеки в бактериальных искусственных хромосомах (BAC), которые предоставили лучшие векторы для молекулярного клонирования . [20]
Достижения в области биоинформатики , совершенствование амплификации ДНК и распространение вычислительных мощностей во многом помогли анализу последовательностей ДНК, извлеченных из образцов окружающей среды, что позволило адаптировать метод дробового секвенирования к метагеномным образцам (известный также как дробовое секвенирование полного метагенома или секвенирование WMGS). Этот подход, используемый для секвенирования многих культивируемых микроорганизмов и генома человека , случайным образом разрезает ДНК, секвенирует множество коротких последовательностей и реконструирует их в консенсусную последовательность . Секвенирование методом дробовика выявляет гены, присутствующие в образцах окружающей среды. Исторически для облегчения такого секвенирования использовались библиотеки клонов. Однако с развитием технологий высокопроизводительного секвенирования этап клонирования больше не нужен, и больший выход данных секвенирования можно получить без этого трудоемкого этапа. Метагеномика дробовика предоставляет информацию как о том, какие организмы присутствуют, так и о том, какие метаболические процессы возможны в сообществе. [21] Поскольку сбор ДНК из окружающей среды практически не контролируется, наиболее распространенные организмы в образце из окружающей среды наиболее широко представлены в результирующих данных о последовательностях. Для достижения высокого охвата, необходимого для полного определения геномов недостаточно представленных членов сообщества, необходимы большие выборки, часто непомерно высокие. С другой стороны, случайный характер дробового секвенирования гарантирует, что многие из этих организмов, которые в противном случае остались бы незамеченными при использовании традиционных методов культивирования, будут представлены по крайней мере несколькими небольшими сегментами последовательности. [13]
Преимущество высокопроизводительного секвенирования заключается в том, что этот метод не требует клонирования ДНК перед секвенированием, что устраняет одну из основных ошибок и узких мест при отборе проб окружающей среды. Первые метагеномные исследования, проведенные с использованием высокопроизводительного секвенирования, использовали массовое параллельное пиросеквенирование 454 . [17] Еще три технологии, обычно применяемые для отбора проб окружающей среды, — это персональная геномная машина Ion Torrent , Illumina MiSeq или HiSeq и система SOLiD компании Applied Biosystems . [22] Эти методы секвенирования ДНК позволяют получить более короткие фрагменты, чем секвенирование по Сэнгеру ; Система Ion Torrent PGM и пиросеквенирование 454 обычно производят считывания размером ~400 п.н., Illumina MiSeq производит считывания 400–700 п.н. (в зависимости от того, используются ли варианты с парными концами), а SOLiD производит считывания 25–75 п.н. [23] Исторически эти длины чтения были значительно короче, чем типичная длина чтения секвенирования Сэнгера, составляющая ~ 750 п.о., однако технология Illumina быстро приближается к этому эталону. Однако это ограничение компенсируется гораздо большим количеством считываний последовательности. В 2009 году пиросеквенированные метагеномы генерировали 200–500 мегабаз, а платформы Illumina генерировали около 20–50 гигабаз, но в последние годы эти результаты увеличились на порядки. [24]
Новый подход сочетает в себе дробовое секвенирование и захват конформации хромосом (Hi-C), который измеряет близость любых двух последовательностей ДНК в одной и той же клетке, чтобы управлять сборкой микробного генома. [25] Технологии секвенирования длинных считываний, в том числе PacBio RSII и PacBio Sequel от Pacific Biosciences , а также Nanopore MinION, GridION, PromethION от Oxford Nanopore Technologies , являются еще одним выбором для получения длинных считываний секвенирования, которые должны облегчить процесс сборки. [26]
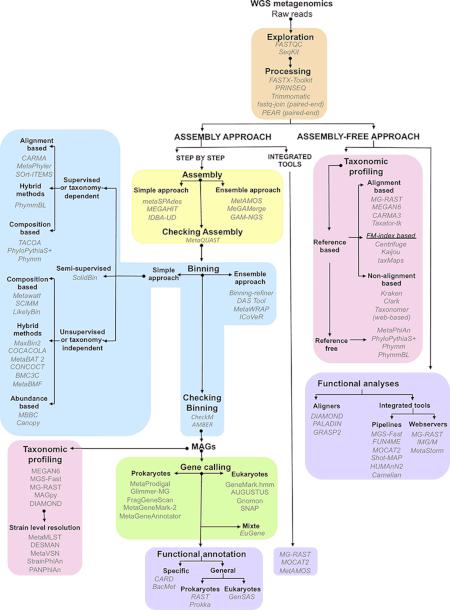
Данные, полученные в ходе экспериментов по метагеномике, огромны и по своей сути зашумлены: они содержат фрагментированные данные, представляющие до 10 000 видов. [1] Секвенирование метагенома рубца коровы позволило получить 279 гигабаз , или 279 миллиардов пар оснований данных о последовательностях нуклеотидов, [28] в то время как каталог генов микробиома кишечника человека идентифицировал 3,3 миллиона генов, собранных из 567,7 гигабаз данных о последовательностях. [29] Сбор, обработка и извлечение полезной биологической информации из наборов данных такого размера представляют собой значительные вычислительные проблемы для исследователей. [21] [30] [31] [32]
Первый этап анализа метагеномных данных требует выполнения определенных этапов предварительной фильтрации, включая удаление избыточных последовательностей низкого качества и последовательностей вероятного эукариотического происхождения (особенно в метагеномах человеческого происхождения). [33] [34] Доступные методы удаления загрязняющих последовательностей геномной ДНК эукариот включают Eu-Detect и DeConseq. [35] [36]
Данные о последовательностях ДНК из геномных и метагеномных проектов по существу одинаковы, но данные о геномных последовательностях обеспечивают более широкий охват , в то время как метагеномные данные обычно не являются избыточными. [31] Более того, более широкое использование технологий секвенирования второго поколения с короткой длиной считывания означает, что большая часть будущих метагеномных данных будет подвержена ошибкам. В совокупности эти факторы делают сборку считывания метагеномных последовательностей в геномах сложной и ненадежной. Неправильная сборка вызвана наличием повторяющихся последовательностей ДНК , которые особенно затрудняют сборку из-за разницы в относительном обилии видов, присутствующих в образце. [37] Неправильная сборка может также включать объединение последовательностей более чем одного вида в химерные контиги . [37]
Существует несколько программ сборки, большинство из которых могут использовать информацию из парных тегов для повышения точности сборки. Некоторые программы, такие как Phrap или Celera Assembler, были разработаны для сборки отдельных геномов , но, тем не менее, дают хорошие результаты при сборке наборов метагеномных данных. [1] Другие программы, такие как ассемблер Velvet , были оптимизированы для более коротких чтений, производимых секвенированием второго поколения с использованием графов де Брейна . [38] [39] Использование эталонных геномов позволяет исследователям улучшить сборку наиболее распространенных видов микробов, но этот подход ограничен небольшим подмножеством типов микробов, для которых доступны секвенированные геномы. [37] После создания сборки дополнительной задачей является «метагеномная деконволюция» или определение того, какие последовательности принадлежат каким видам в образце. [40]
Конвейеры метагеномного анализа используют два подхода к аннотации кодирующих областей в собранных контигах. [37] Первый подход заключается в идентификации генов на основе гомологии с генами, которые уже общедоступны в базах данных последовательностей , обычно с помощью поиска BLAST . Этот тип подхода реализован в программе MEGAN 4. [41] Второй, ab initio , использует внутренние особенности последовательности для прогнозирования кодирующих областей на основе обучающих наборов генов родственных организмов. Именно этот подход используется в таких программах, как GeneMark [42] и GLIMMER . Основное преимущество предсказания ab initio состоит в том, что оно позволяет обнаруживать кодирующие области, у которых отсутствуют гомологи в базах данных последовательностей; однако он наиболее точен, когда для сравнения доступны большие участки смежной геномной ДНК. [1]
Генные аннотации дают ответ «что», а измерения видового разнообразия дают ответ «кто». [43] Чтобы связать состав сообщества и функцию в метагеномах, последовательности должны быть объединены. Биннинг — это процесс связывания определенной последовательности с организмом. [37] При объединении на основе сходства такие методы, как BLAST , используются для быстрого поиска филогенетических маркеров или других подобных последовательностей в существующих общедоступных базах данных. Такой подход реализован в МЕГАН . [44] Другой инструмент, PhymmBL, использует интерполированные модели Маркова для назначения показаний. [1] MetaPhlAn и AMPHORA — это методы, основанные на уникальных маркерах, специфичных для клады, для оценки относительной численности организмов с улучшенными вычислительными характеристиками. [45] Другие инструменты, такие как mOTUs [46] [47] и MetaPhyler [48] , используют универсальные маркерные гены для профилирования видов прокариот. С помощью профилировщика mOTUs можно составлять профили видов без эталонного генома, что улучшает оценку разнообразия микробного сообщества. [47] Последние методы, такие как SLIMM, используют ландшафт покрытия чтения отдельных эталонных геномов, чтобы минимизировать ложноположительные совпадения и получить надежную относительную численность. [49] При биннинге на основе композиции методы используют внутренние особенности последовательности, такие как частоты олигонуклеотидов или систематическая ошибка использования кодонов . [1] После группирования последовательностей можно провести сравнительный анализ разнообразия и богатства.
Огромный объем экспоненциально растущих данных о последовательностях представляет собой сложную задачу, которая осложняется сложностью метаданных, связанных с метагеномными проектами. Метаданные включают подробную информацию о трехмерной (включая глубину или высоту) географии и характеристиках окружающей среды образца, физических данных о месте отбора проб и методологии отбора проб. [31] Эта информация необходима как для обеспечения воспроизводимости , так и для последующего анализа. Из-за своей важности метаданные, а также совместный анализ и обработка данных требуют стандартизированных форматов данных, расположенных в специализированных базах данных, таких как база данных Genomes OnLine Database (GOLD). [50]
Было разработано несколько инструментов для интеграции метаданных и данных о последовательностях, что позволяет проводить последующий сравнительный анализ различных наборов данных с использованием ряда экологических индексов. В 2007 году Фолкер Мейер и Роберт Эдвардс и команда Аргоннской национальной лаборатории и Чикагского университета выпустили «Быструю аннотацию метагеномики с использованием сервера Subsystem Technology» ( MG-RAST ) — ресурс сообщества для анализа наборов метагеномных данных. [51] По состоянию на июнь 2012 года было проанализировано более 14,8 терабаз (14x10 12 оснований) ДНК, при этом более 10 000 общедоступных наборов данных свободно доступны для сравнения в рамках MG-RAST. В настоящее время более 8000 пользователей отправили в MG-RAST в общей сложности 50 000 метагеномов. Система «Интегрированные микробные геномы/метагеномы» (IMG/M) также предоставляет набор инструментов для функционального анализа микробных сообществ на основе их метагеномной последовательности, основанной на эталонных геномах изолятов, включенных в систему «Интегрированные микробные геномы» (IMG) и Геномную энциклопедию Проект «Бактерии и археи» (GEBA). [52]
Одним из первых автономных инструментов для анализа метагеномных данных с высокой пропускной способностью был MEGAN (MEta Genome ANalyzer). [41] [44] Первая версия программы была использована в 2005 году для анализа метагеномного контекста последовательностей ДНК, полученных из кости мамонта. [17] На основе сравнения BLAST со справочной базой данных этот инструмент выполняет как таксономическое, так и функциональное группирование, помещая чтения в узлы таксономии NCBI с использованием простого алгоритма наименьшего общего предка (LCA) или в узлы SEED. или классификации KEGG соответственно. [53]
С появлением быстрых и недорогих инструментов секвенирования рост баз данных последовательностей ДНК стал экспоненциальным (например, база данных NCBI GenBank [54] ). Чтобы идти в ногу с высокопроизводительным секвенированием, необходимы более быстрые и эффективные инструменты, поскольку подходы на основе BLAST, такие как MG-RAST или MEGAN, работают медленно для аннотирования больших образцов (например, несколько часов для обработки набора данных/образца небольшого/среднего размера). [55] ). Так, в последнее время появились сверхбыстрые классификаторы благодаря более доступным мощным серверам. Эти инструменты могут выполнять таксономическую аннотацию с чрезвычайно высокой скоростью, например CLARK [56] (по словам авторов CLARK, он может точно классифицировать «32 миллиона метагеномных коротких чтений в минуту»). При такой скорости очень большой набор данных/выборка из миллиарда коротких чтений может быть обработан примерно за 30 минут.
С увеличением доступности образцов, содержащих древнюю ДНК, и из-за неопределенности, связанной с природой этих образцов (повреждение древней ДНК), [57] стал доступен быстрый инструмент, способный производить консервативные оценки сходства. По словам авторов FALCON, он может использовать смягченные пороги и редактировать расстояния, не влияя на память и скорость работы.
Сравнительный анализ метагеномов может дать дополнительное представление о функции сложных микробных сообществ и их роли в здоровье хозяина. [58] Парные или множественные сравнения метагеномов могут проводиться на уровне состава последовательностей (сравнение содержания GC или размера генома), таксономического разнообразия или функционального комплемента. Сравнение популяционной структуры и филогенетического разнообразия можно проводить на основе 16S рРНК и других генов-филогенетических маркеров или, в случае сообществ с низким разнообразием, путем реконструкции генома по набору метагеномных данных. [59] Функциональные сравнения между метагеномами могут быть выполнены путем сравнения последовательностей со справочными базами данных, такими как COG или KEGG , а также составления таблиц обилия по категориям и оценки любых различий на предмет статистической значимости. [53] Этот геноцентричный подход подчеркивает функциональный состав сообщества в целом, а не таксономических групп, и показывает, что функциональные дополнения аналогичны в аналогичных условиях окружающей среды. [59] Следовательно, метаданные об экологическом контексте метагеномного образца особенно важны в сравнительном анализе, поскольку они дают исследователям возможность изучать влияние среды обитания на структуру и функционирование сообщества. [1]
Кроме того, в нескольких исследованиях также использовались модели использования олигонуклеотидов для выявления различий между различными микробными сообществами. Примеры таких методологий включают подход относительного содержания динуклеотидов Willner et al. [60] и подход HabiSign Ghosh et al. [61] Это последнее исследование также показало, что различия в моделях использования тетрануклеотидов могут быть использованы для идентификации генов (или метагеномных чтений), происходящих из конкретных сред обитания. Кроме того, некоторые методы, такие как TriageTools [62] или Compareads [63], обнаруживают схожие операции чтения между двумя наборами операций чтения. Мера сходства , которую они применяют при чтении, основана на количестве идентичных слов длины k , общих для пар чтений.
Ключевой целью сравнительной метагеномики является идентификация микробных групп, которые отвечают за придание определенных характеристик данной среде. Однако из-за проблем в технологиях секвенирования необходимо учитывать артефакты, как в MetagenomeSeq. [30] Другие охарактеризовали межмикробные взаимодействия между резидентными микробными группами. Приложение сравнительного метагеномного анализа на основе графического пользовательского интерфейса под названием Community-Analyzer было разработано Kuntal et al. [64] , в котором реализован алгоритм построения графов на основе корреляции, который не только облегчает быструю визуализацию различий в анализируемых микробных сообществах (с точки зрения их таксономического состава), но также дает представление о присущих им межмикробных взаимодействиях, происходящих в них. Примечательно, что этот алгоритм компоновки также позволяет группировать метагеномы на основе вероятных моделей межмикробного взаимодействия, а не просто сравнивать значения численности различных таксономических групп. Кроме того, инструмент реализует несколько интерактивных функций на основе графического пользовательского интерфейса, которые позволяют пользователям выполнять стандартный сравнительный анализ микробиомов.
Во многих бактериальных сообществах, природных или искусственно созданных (например, в биореакторах ), существует значительное разделение труда в метаболизме ( синтрофия ), в ходе которого продукты жизнедеятельности одних организмов являются метаболитами для других. [65] В одной из таких систем, метаногенном биореакторе, функциональная стабильность требует присутствия нескольких синтрофных видов ( Syntropobacterales и Synergistia ), работающих вместе, чтобы превратить сырьевые ресурсы в полностью метаболизированные отходы ( метан ). [66] Используя сравнительные исследования генов и эксперименты по экспрессии с использованием микрочипов или протеомики , исследователи могут собрать воедино метаболическую сеть, выходящую за рамки видовых границ. Такие исследования требуют детальных знаний о том, какие версии каких белков кодируются какими видами и даже какими штаммами каких видов. Таким образом, геномная информация сообщества является еще одним фундаментальным инструментом (наряду с метаболомикой и протеомикой) в поисках определения того, как метаболиты передаются и трансформируются сообществом. [67]
Метагеномика позволяет исследователям получить доступ к функциональному и метаболическому разнообразию микробных сообществ, но не может показать, какие из этих процессов активны. [59] Извлечение и анализ метагеномной мРНК ( метатранскриптома ) предоставляет информацию о профилях регуляции и экспрессии сложных сообществ. Из-за технических трудностей ( например, короткого периода полураспада мРНК) при сборе РНК из окружающей среды на сегодняшний день было проведено относительно мало метатранскриптомных исследований микробных сообществ in situ . [59] Хотя первоначально исследования метатранскриптомики ограничивались технологией микрочипов , в исследованиях метатранскриптомики использовались технологии транскриптомики для измерения полногеномной экспрессии и количественной оценки микробного сообщества, [59] впервые использованные при анализе окисления аммиака в почвах. [68]
Метагеномное секвенирование особенно полезно при изучении вирусных сообществ. Поскольку у вирусов нет общего универсального филогенетического маркера (например, 16S РНК для бактерий и архей и 18S РНК для эукарий), единственный способ получить доступ к генетическому разнообразию вирусного сообщества из образца окружающей среды — это метагеномика. Таким образом, вирусные метагеномы (также называемые виромами) должны предоставлять все больше и больше информации о вирусном разнообразии и эволюции. [69] [70] [71] [72] [73] Например, метагеномный конвейер под названием Giant Virus Finder показал первые доказательства существования гигантских вирусов в солончаковой пустыне [74] и в сухих долинах Антарктики. [75]
Метагеномика обладает потенциалом для развития знаний в самых разных областях. Его также можно применять для решения практических задач в медицине , инженерии , сельском хозяйстве , устойчивом развитии и экологии . [31] [76]
Почвы , на которых растут растения, населены микробными сообществами: один грамм почвы содержит около 10 9 -10 10 микробных клеток, которые содержат около одной гигабазы информации о последовательностях. [77] [78] Микробные сообщества, населяющие почвы, являются одними из самых сложных, известных науке, и остаются плохо изученными, несмотря на их экономическое значение. [79] Микробные консорциумы выполняют широкий спектр экосистемных услуг, необходимых для роста растений, включая фиксацию атмосферного азота , круговорот питательных веществ , подавление болезней и связывание железа и других металлов . [80] Стратегии функциональной метагеномики используются для изучения взаимодействия между растениями и микробами посредством независимого от культивирования изучения этих микробных сообществ. [81] [82] Позволяя понять роль ранее некультивируемых или редких членов сообщества в круговороте питательных веществ и стимулировании роста растений, метагеномные подходы могут способствовать улучшению выявления болезней сельскохозяйственных культур и домашнего скота и адаптации улучшенных методов ведения сельского хозяйства , которые улучшают здоровье сельскохозяйственных культур, используя взаимосвязь между микробами и растениями. [31]
Биотопливо — это топливо , полученное в результате переработки биомассы , например, при преобразовании целлюлозы , содержащейся в стеблях кукурузы , просе и другой биомассе, в целлюлозный этанол . [31] Этот процесс зависит от микробных консорциумов (ассоциаций), которые преобразуют целлюлозу в сахара с последующей ферментацией сахаров в этанол . Микробы также производят различные источники биоэнергии , включая метан и водород . [31]
Эффективное разрушение биомассы в промышленных масштабах требует новых ферментов с более высокой производительностью и меньшей стоимостью. [28] Метагеномные подходы к анализу сложных микробных сообществ позволяют целенаправленно проверять ферменты , имеющие промышленное применение в производстве биотоплива, такие как гликозидгидролазы . [83] Кроме того, для контроля над ними необходимы знания о том, как функционируют эти микробные сообщества, и метагеномика является ключевым инструментом в их понимании. Метагеномные подходы позволяют проводить сравнительный анализ конвергентных микробных систем, таких как биогазовые ферментеры [84] или травоядных насекомых , таких как грибной сад муравьев- листорезов . [85]
Микробные сообщества производят широкий спектр биологически активных химических веществ, которые используются в конкуренции и общении. [80] Многие из используемых сегодня лекарств изначально были обнаружены в микробах; недавний прогресс в разработке богатого генетического ресурса некультивируемых микробов привел к открытию новых генов, ферментов и натуральных продуктов. [59] [86] Применение метагеномики позволило разработать товарные и тонкие химикаты , агрохимикаты и фармацевтические препараты , где все больше признается польза хирального синтеза , катализируемого ферментами . [87]
При биоразведке метагеномных данных используются два типа анализа : функциональный скрининг выраженного признака и скрининг на основе последовательности интересующих последовательностей ДНК. [88] Функционально-ориентированный анализ направлен на идентификацию клонов, проявляющих желаемый признак или полезную активность, с последующей биохимической характеристикой и анализом последовательности. Этот подход ограничен наличием подходящего скрининга и требованием экспрессии желаемого признака в клетке-хозяине. Более того, низкий уровень обнаружения (менее одного на 1000 проверенных клонов) и трудоемкий характер еще больше ограничивают этот подход. [89] Напротив, анализ, основанный на последовательностях, использует консервативные последовательности ДНК для разработки праймеров для ПЦР для скрининга клонов на предмет интересующей последовательности. [88] По сравнению с подходами, основанными на клонировании, использование подхода, основанного только на последовательностях, еще больше снижает объем необходимой лабораторной работы. Применение массово-параллельного секвенирования также значительно увеличивает объем генерируемых данных о последовательностях, что требует высокопроизводительных конвейеров биоинформатического анализа. [89] Подход к скринингу, основанный на последовательностях, ограничен широтой и точностью функций генов, представленных в общедоступных базах данных последовательностей. На практике в экспериментах используется комбинация функционального и последовательностного подходов, основанная на интересующей функции, сложности проверяемого образца и других факторах. [89] [90] Примером успеха использования метагеномики в качестве биотехнологии для открытия лекарств является антибиотик малацидин . [91]

Метагеномика может дать ценную информацию о функциональной экологии экологических сообществ. [92] Метагеномный анализ бактериальных консорциумов, обнаруженных в испражнениях австралийских морских львов, позволяет предположить, что богатые питательными веществами фекалии морских львов могут быть важным источником питательных веществ для прибрежных экосистем. Это связано с тем, что бактерии, которые выделяются одновременно с дефекацией, способны расщеплять питательные вещества, содержащиеся в фекалиях, в биодоступную форму, которая может быть использована в пищевой цепи. [93]
Секвенирование ДНК также можно использовать в более широком смысле для идентификации видов, присутствующих в водоеме, [94] мусоре, отфильтрованном из воздуха, образцах грязи или фекалиях животных, [95] и даже для обнаружения продуктов питания из крови. [96] Это позволяет установить ареал инвазивных видов и видов, находящихся под угрозой исчезновения , а также отслеживать сезонные популяции.
Метагеномика может улучшить стратегии мониторинга воздействия загрязнителей на экосистемы и очистки загрязненной окружающей среды. Более глубокое понимание того, как микробные сообщества справляются с загрязнителями, улучшает оценку потенциала загрязненных территорий для восстановления после загрязнения и увеличивает шансы на успех испытаний биоаугментации или биостимуляции . [97]
Микробные сообщества играют ключевую роль в сохранении здоровья человека , но их состав и механизм, с помощью которого они это делают, остаются загадкой. [98] Метагеномное секвенирование используется для характеристики микробных сообществ из 15–18 участков тела как минимум 250 человек. Это часть инициативы «Микробиом человека», основная цель которой — определить, существует ли основной микробиом человека , понять изменения в микробиоме человека, которые можно коррелировать со здоровьем человека, а также разработать новые технологические и биоинформатические инструменты для поддержки этих целей. [99]
В другом медицинском исследовании в рамках проекта MetaHit (Метагеномика кишечного тракта человека) приняли участие 124 человека из Дании и Испании, состоящие из здоровых пациентов с избыточным весом и раздраженным кишечником. [100] В исследовании была предпринята попытка классифицировать глубину и филогенетическое разнообразие желудочно-кишечных бактерий. Используя данные последовательности Illumina GA и SOAPdenovo, инструмент на основе графов де Брейна, специально разработанный для коротких чтений сборки, они смогли сгенерировать 6,58 миллиона контигов размером более 500 пар оснований с общей длиной контига 10,3 ГБ и длиной N50 2,2 КБ.
Исследование показало, что два бактериальных подразделения, Bacteroidetes и Firmicutes, составляют более 90% известных филогенетических категорий, которые доминируют в бактериях дистальных отделов кишечника. Используя относительные частоты генов, обнаруженных в кишечнике, исследователи определили 1244 метагеномных кластера, которые критически важны для здоровья кишечного тракта. В этих кластерах диапазонов выделяются два типа функций: хозяйственные и специфичные для кишечника. Кластеры генов «домашнего хозяйства» необходимы всем бактериям и часто играют важную роль в основных метаболических путях, включая центральный метаболизм углерода и синтез аминокислот. Специфические для кишечника функции включают адгезию к белкам хозяина и сбор сахаров из гликолипидов шаровидного ряда. Было показано, что у пациентов с синдромом раздраженного кишечника наблюдается на 25% меньше генов и меньшее бактериальное разнообразие, чем у людей, не страдающих синдромом раздраженного кишечника, что указывает на то, что изменения в разнообразии биома кишечника пациентов могут быть связаны с этим заболеванием. [100]
Хотя эти исследования подчеркивают некоторые потенциально ценные медицинские применения, только 31–48,8% чтений могут быть сопоставлены со 194 общедоступными бактериальными геномами кишечника человека и 7,6–21,2% с бактериальными геномами, доступными в GenBank, что указывает на то, что необходимо еще гораздо больше исследований, чтобы захватывать новые бактериальные геномы. [101]
В рамках проекта «Микробиом человека» (HMP) микробные сообщества кишечника анализировались с использованием высокопроизводительного секвенирования ДНК. HMP показал, что, в отличие от отдельных видов микробов, многие метаболические процессы присутствуют во всех средах обитания организма с различной частотой. В рамках проекта микробиома человека были изучены микробные сообщества 649 метагеномов, взятых из семи первичных участков тела 102 человек . Метагеномный анализ выявил различия в специфическом количестве ниш среди 168 функциональных модулей и 196 метаболических путей внутри микробиома. Они включали деградацию гликозаминогликанов в кишечнике, а также транспорт фосфатов и аминокислот, связанный с фенотипом хозяина (рН влагалища) в заднем своде. HMP выявил полезность метагеномики в диагностике и доказательной медицине . Таким образом, метагеномика является мощным инструментом для решения многих актуальных проблем в области персонализированной медицины . [102]
У животных метагеномика может использоваться для составления профиля микробиома кишечника и обнаружения бактерий, устойчивых к антибиотикам. [103] Это может иметь значение для мониторинга распространения болезней от диких животных к сельскохозяйственным животным и людям.
Дифференциация инфекционных и неинфекционных заболеваний и выявление основной этиологии инфекции может быть сложной задачей. Например, более половины случаев энцефалита остаются недиагностированными, несмотря на обширное тестирование с использованием самых современных клинических лабораторных методов. Клиническое метагеномное секвенирование перспективно в качестве чувствительного и быстрого метода диагностики инфекции путем сравнения генетического материала, обнаруженного в образце пациента, с базами данных всех известных микроскопических патогенов человека и тысяч других бактериальных, вирусных, грибковых и паразитических организмов, а также базами данных по генам устойчивости к противомикробным препаратам. последовательности с соответствующими клиническими фенотипами. [104]
Метагеномика стала бесценным инструментом, помогающим охарактеризовать разнообразие и экологию патогенов, переносчиками которых являются гематофаги (кровопитающиеся) насекомые, такие как комары и клещи. [105] [106] [107] Метагеномика — это [ когда? ] регулярно используется должностными лицами и организациями общественного здравоохранения [ где? ] для надзора за арбовирусами . [108] [109]