Folding@home ( FAH или F@h ) — это проект распределенных вычислений , призванный помочь ученым разрабатывать новые терапевтические средства для различных заболеваний с помощью моделирования динамики белков . Это включает в себя процесс сворачивания белков и движения белков , и основано на моделировании, запущенном на персональных компьютерах добровольцев . [5] В настоящее время Folding@home базируется в Университете Пенсильвании и возглавляется Грегом Боуманом, бывшим студентом Виджая Панде . [6]
Проект использует графические процессоры (GPU), центральные процессоры (CPU) и процессоры ARM , подобные тем, что есть на Raspberry Pi, для распределенных вычислений и научных исследований. Проект использует статистическую методологию моделирования , которая является сдвигом парадигмы от традиционных методов вычислений. [7] В рамках сетевой архитектуры клиент-серверной модели каждая из добровольно задействованных машин получает части моделирования (рабочие единицы), завершает их и возвращает на серверы базы данных проекта , где единицы компилируются в общую симуляцию. Добровольцы могут отслеживать свой вклад на веб-сайте Folding@home, что делает участие волонтеров конкурентоспособным и поощряет долгосрочное участие.
Folding@home — одна из самых быстрых вычислительных систем в мире. С возросшим интересом к проекту в результате пандемии COVID - 19 [8] система достигла скорости приблизительно 1,22 экзафлопс к концу марта 2020 года и достигла 2,43 экзафлопс к 12 апреля 2020 года [9] , что сделало ее первой в мире экзафлопсной вычислительной системой . Такой уровень производительности ее крупномасштабной вычислительной сети позволил исследователям запускать вычислительно затратное моделирование сворачивания белка на атомном уровне в тысячи раз дольше, чем это было достигнуто ранее. С момента своего запуска 1 октября 2000 года Folding@home участвовала в создании 226 научно-исследовательских работ [10] Результаты моделирования проекта хорошо согласуются с экспериментами. [ 11] [12] [13]

Белки являются важным компонентом многих биологических функций и участвуют практически во всех процессах в биологических клетках . Они часто действуют как ферменты , выполняя биохимические реакции, включая клеточную сигнализацию , молекулярный транспорт и клеточную регуляцию . Как структурные элементы, некоторые белки действуют как тип скелета для клеток и как антитела , в то время как другие белки участвуют в иммунной системе . Прежде чем белок сможет взять на себя эти роли, он должен свернуться в функциональную трехмерную структуру , процесс, который часто происходит спонтанно и зависит от взаимодействий в его аминокислотной последовательности и взаимодействий аминокислот с их окружением. Сворачивание белка обусловлено поиском наиболее энергетически выгодной конформации белка, т. е. его нативного состояния . Таким образом, понимание сворачивания белка имеет решающее значение для понимания того, что делает белок и как он работает, и считается святым Граалем вычислительной биологии . [14] [15] Несмотря на то, что сворачивание происходит в переполненной клеточной среде , оно обычно происходит гладко. Однако из-за химических свойств белка или других факторов белки могут неправильно сворачиваться , то есть сворачиваться по неправильному пути и в конечном итоге деформироваться. Если клеточные механизмы не могут разрушить или перевернуть неправильно свернутые белки, они могут впоследствии агрегировать и вызывать различные изнурительные заболевания. [16] Лабораторные эксперименты, изучающие эти процессы, могут быть ограничены по масштабу и атомным деталям, что заставляет ученых использовать физические вычислительные модели, которые, дополняя эксперименты, стремятся предоставить более полную картину сворачивания, неправильного сворачивания и агрегации белков. [17] [18]
Из-за сложности пространства конформации или конфигурации белков (набора возможных форм, которые может принимать белок) и ограничений вычислительной мощности, моделирование молекулярной динамики всех атомов было сильно ограничено во временных масштабах, которые они могли изучать. В то время как большинство белков обычно сворачиваются в порядке миллисекунд, [17] [19] до 2010 года моделирование могло достигать только временных масштабов от наносекунд до микросекунд. [11] Для моделирования сворачивания белков использовались суперкомпьютеры общего назначения , но такие системы по своей сути являются дорогостоящими и, как правило, используются многими исследовательскими группами. Кроме того, поскольку вычисления в кинетических моделях происходят последовательно, сильное масштабирование традиционных молекулярных симуляций для этих архитектур исключительно сложно. [20] [21] Более того, поскольку сворачивание белка является стохастическим процессом (т. е. случайным) и может статистически изменяться со временем, с вычислительной точки зрения сложно использовать длительные симуляции для всесторонних представлений о процессе сворачивания. [22] [23]
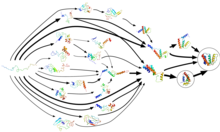
Сворачивание белка не происходит за один шаг. [16] Вместо этого белки проводят большую часть времени сворачивания, в некоторых случаях почти 96%, [24] ожидая в различных промежуточных конформационных состояниях, каждое из которых является локальным термодинамическим минимумом свободной энергии в энергетическом ландшафте белка . Благодаря процессу, известному как адаптивная выборка , эти конформации используются Folding@home в качестве отправных точек для набора траекторий моделирования. По мере того, как моделирование обнаруживает больше конформаций, траектории перезапускаются с них, и из этого циклического процесса постепенно создается модель состояния Маркова (MSM). MSM представляют собой модели основных уравнений с дискретным временем , которые описывают конформационный и энергетический ландшафт биомолекулы как набор отдельных структур и коротких переходов между ними. Метод модели состояния Маркова с адаптивной выборкой значительно повышает эффективность моделирования, поскольку он избегает вычислений внутри самого локального минимума энергии и поддается распределенным вычислениям (в том числе на GPUGRID ), поскольку он позволяет проводить статистическую агрегацию коротких независимых траекторий моделирования. [25] Количество времени, необходимое для построения модели марковских состояний, обратно пропорционально количеству запущенных параллельных симуляций, т. е. количеству доступных процессоров. Другими словами, достигается линейное распараллеливание , что приводит к сокращению общего времени последовательных вычислений примерно на четыре порядка . Завершенная MSM может содержать десятки тысяч состояний образцов из фазового пространства белка (все конформации, которые может принимать белок) и переходы между ними. Модель иллюстрирует события и пути сворачивания (т. е. маршруты), и исследователи могут позже использовать кинетическую кластеризацию для просмотра грубозернистого представления в противном случае высокодетализированной модели. Они могут использовать эти MSM, чтобы выявить, как белки неправильно сворачиваются, и количественно сравнить симуляции с экспериментами. [7] [22] [26]
В период с 2000 по 2010 год длина белков, которые изучал Folding@home, увеличилась в четыре раза, в то время как временные рамки для моделирования сворачивания белков увеличились на шесть порядков. [27] В 2002 году Folding@home использовала модели марковских состояний для завершения примерно миллиона процессорных дней моделирования в течение нескольких месяцев, [13] а в 2011 году MSM распараллелила другое моделирование, которое потребовало в общей сложности 10 миллионов процессорных часов вычислений. [28] В январе 2010 года Folding@home использовала MSM для моделирования динамики медленно сворачивающегося 32- остаточного белка NTL9 до 1,52 миллисекунд, временные рамки согласуются с экспериментальными предсказаниями скорости сворачивания, но в тысячу раз длиннее, чем достигалось ранее. Модель состояла из множества отдельных траекторий, каждая на два порядка короче, и обеспечивала беспрецедентный уровень детализации энергетического ландшафта белка. [7] [11] [29] В 2010 году исследователь Folding@home Грегори Боуман был награжден премией Томаса Куна Paradigm Shift Award от Американского химического общества за разработку программного обеспечения с открытым исходным кодом MSMBuilder и за достижение количественного согласия между теорией и экспериментом. [30] [31] За свою работу Панде был награжден премией Майкла и Кейт Барани для молодых исследователей 2012 года за «разработку определяющих и изменяющих поле вычислительных методов для создания ведущих теоретических моделей сворачивания белков и РНК » [32] и премией Ирвинга Сигала для молодых исследователей 2006 года за его результаты моделирования, которые «стимулировали переосмысление значения как ансамблевых, так и одиночных молекулярных измерений, сделав усилия Панде пионерским вкладом в методологию моделирования». [33]
Неправильное сворачивание белка может привести к различным заболеваниям , включая болезнь Альцгеймера, рак , болезнь Крейтцфельдта-Якоба , муковисцидоз , болезнь Хантингтона, серповидноклеточную анемию и диабет II типа . [16] [34] [35] Клеточная инфекция вирусами, такими как ВИЧ и грипп, также включает события сворачивания на клеточных мембранах . [36] Как только неправильное сворачивание белка будет лучше понято, могут быть разработаны методы лечения, которые усиливают естественную способность клеток регулировать сворачивание белка. Такие методы лечения включают использование сконструированных молекул для изменения производства данного белка, помощи в разрушении неправильно свернутого белка или содействия процессу сворачивания. [37] Сочетание вычислительного молекулярного моделирования и экспериментального анализа имеет возможность фундаментально сформировать будущее молекулярной медицины и рационального дизайна терапевтических средств , [18] например, ускорения и снижения затрат на открытие лекарств . [38] Целью первых пяти лет проекта Folding@home было достижение прогресса в понимании процесса складывания, в то время как нынешняя цель — понять неправильное складывание и связанные с ним заболевания, особенно болезнь Альцгеймера. [39]
Моделирование, запущенное на Folding@home, используется в сочетании с лабораторными экспериментами, [22], но исследователи могут использовать его для изучения того, как сворачивание in vitro отличается от сворачивания в нативной клеточной среде. Это выгодно при изучении аспектов сворачивания, неправильного сворачивания и их связи с болезнями, которые трудно наблюдать экспериментально. Например, в 2011 году Folding@home смоделировал сворачивание белка внутри выходного туннеля рибосомы , чтобы помочь ученым лучше понять, как естественное ограничение и скученность могут влиять на процесс сворачивания. [40] [41] Кроме того, ученые обычно используют химические денатуранты для разворачивания белков из их стабильного нативного состояния. Неизвестно, как денатурант влияет на повторное сворачивание белка, и трудно экспериментально определить, содержат ли эти денатурированные состояния остаточные структуры, которые могут влиять на поведение сворачивания. В 2010 году Folding@home использовал графические процессоры для моделирования развернутых состояний белка L и предсказал скорость его коллапса в строгом соответствии с экспериментальными результатами. [42]
Большие наборы данных из проекта доступны для свободного использования другими исследователями по запросу, а некоторые из них можно получить на веб-сайте Folding@home. [43] [44] Лаборатория Панде сотрудничала с другими системами молекулярной динамики, такими как суперкомпьютер Blue Gene , [45] и они делятся ключевым программным обеспечением Folding@home с другими исследователями, так что алгоритмы, которые принесли пользу Folding@home, могут помочь другим научным областям. [43] В 2011 году они выпустили программное обеспечение Copernicus с открытым исходным кодом, которое основано на MSM Folding@home и других методах распараллеливания и направлено на повышение эффективности и масштабирования молекулярных симуляций на больших компьютерных кластерах или суперкомпьютерах . [46] [47] Резюме всех научных результатов Folding@home публикуются на веб-сайте Folding@home после публикации. [48]
Болезнь Альцгеймера — неизлечимое нейродегенеративное заболевание, которое чаще всего поражает пожилых людей и составляет более половины всех случаев слабоумия . Точная причина заболевания остается неизвестной, но заболевание определяется как болезнь неправильного сворачивания белка . Болезнь Альцгеймера связана с токсичными агрегациями пептида бета-амилоида ( Aβ) , вызванными неправильным сворачиванием Aβ и слипанием с другими пептидами Aβ. Эти агрегаты Aβ затем вырастают в значительно более крупные сенильные бляшки , патологический маркер болезни Альцгеймера. [49] [50] [51] Из-за гетерогенной природы этих агрегатов экспериментальные методы, такие как рентгеновская кристаллография и ядерный магнитный резонанс (ЯМР), столкнулись с трудностями при описании их структур. Более того, атомное моделирование агрегации Aβ требует больших вычислительных затрат из-за их размера и сложности. [52] [53]
Предотвращение агрегации Aβ является перспективным методом разработки терапевтических препаратов для лечения болезни Альцгеймера, согласно Наиму и Фазили в обзорной статье. [54] В 2008 году Folding@home смоделировал динамику агрегации Aβ в атомных деталях в масштабах времени порядка десятков секунд. Предыдущие исследования могли смоделировать только около 10 микросекунд. Folding@home смог смоделировать сворачивание Aβ на шесть порядков дольше, чем это было возможно ранее. Исследователи использовали результаты этого исследования, чтобы идентифицировать бета-шпильку , которая была основным источником молекулярных взаимодействий внутри структуры. [55] Исследование помогло подготовить лабораторию Панде к будущим исследованиям агрегации и к дальнейшим исследованиям по поиску небольшого пептида, который может стабилизировать процесс агрегации. [52]
В декабре 2008 года Folding@home обнаружил несколько небольших кандидатов на лекарственные препараты, которые, по-видимому, подавляют токсичность агрегатов Aβ. [56] В 2010 году в тесном сотрудничестве с Центром машинного сворачивания белков эти препараты начали тестироваться на биологических тканях . [35] В 2011 году Folding@home завершил моделирование нескольких мутаций Aβ, которые, по-видимому, стабилизируют образование агрегатов, что может помочь в разработке терапевтических лекарственных средств для лечения этого заболевания и оказать значительную помощь в экспериментальных исследованиях олигомеров Aβ с помощью ядерной магнитно-резонансной спектроскопии . [53] [57] Позже в том же году Folding@home начал моделирование различных фрагментов Aβ, чтобы определить, как различные природные ферменты влияют на структуру и сворачивание Aβ. [58] [59]
Болезнь Хантингтона — это нейродегенеративное генетическое заболевание , связанное с неправильным сворачиванием и агрегацией белков. Избыточные повторы аминокислоты глутамина на N-конце белка хантингтина вызывают агрегацию, и хотя поведение повторов не полностью изучено, это приводит к снижению когнитивных способностей, связанному с заболеванием. [60] Как и в случае с другими агрегатами, существует сложность в экспериментальном определении его структуры. [61] Ученые используют Folding@home для изучения структуры агрегата белка хантингтина и прогнозирования того, как он образуется, помогая с рациональными методами разработки лекарств, чтобы остановить образование агрегатов. [35] Фрагмент N17 белка хантингтина ускоряет эту агрегацию, и хотя было предложено несколько механизмов, его точная роль в этом процессе остается в значительной степени неизвестной. [62] Folding@home смоделировал этот и другие фрагменты, чтобы прояснить их роль в заболевании. [63] С 2008 года методы разработки лекарств для болезни Альцгеймера были применены к болезни Гентингтона. [35]
Более половины всех известных видов рака связаны с мутациями p53 , белка - супрессора опухолей, присутствующего в каждой клетке, который регулирует клеточный цикл и подает сигналы о гибели клетки в случае повреждения ДНК . Определенные мутации в p53 могут нарушить эти функции, позволяя аномальной клетке продолжать бесконтрольно расти, что приводит к развитию опухолей . Анализ этих мутаций помогает объяснить основные причины рака, связанного с p53. [64] В 2004 году Folding@home использовался для проведения первого молекулярно-динамического исследования рефолдинга димера белка p53 в полностью атомной симуляции воды . Результаты моделирования согласовались с экспериментальными наблюдениями и дали представление о рефолдинге димера, которое ранее было невозможно получить. [65] Это была первая рецензируемая публикация о раке из проекта распределенных вычислений. [66] В следующем году Folding@home разработал новый метод для определения аминокислот, имеющих решающее значение для стабильности данного белка, который затем использовался для изучения мутаций p53. Метод оказался достаточно успешным в выявлении мутаций, способствующих развитию рака, и определил эффекты конкретных мутаций, которые невозможно было измерить экспериментально. [67]
Folding@home также используется для изучения белковых шаперонов , [35] белков теплового шока , которые играют важную роль в выживании клеток, помогая сворачивать другие белки в переполненной и химически стрессовой среде внутри клетки. Быстрорастущие раковые клетки полагаются на определенные шапероны, и некоторые шапероны играют ключевую роль в устойчивости к химиотерапии . Ингибирование этих определенных шаперонов рассматривается как потенциальные способы действия для эффективных химиотерапевтических препаратов или для уменьшения распространения рака. [68] Используя Folding@home и тесно сотрудничая с Центром механизмов сворачивания белков, лаборатория Панде надеется найти лекарство, которое ингибирует эти шапероны, участвующие в раковых клетках. [69] Исследователи также используют Folding@home для изучения других молекул, связанных с раком, таких как фермент Src-киназа и некоторые формы engrailed гомеодомена : большого белка, который может быть вовлечен во многие заболевания, включая рак. [70] [71] В 2011 году Folding@home начал моделирование динамики белка малого узелка EETI, который может идентифицировать карциномы при сканировании изображений путем связывания с поверхностными рецепторами раковых клеток. [72] [73]
Интерлейкин 2 (ИЛ-2) — это белок, который помогает Т-клеткам иммунной системы атаковать патогены и опухоли. Однако его использование в качестве лечения рака ограничено из-за серьезных побочных эффектов, таких как отек легких . ИЛ-2 связывается с этими легочными клетками иначе, чем с Т-клетками, поэтому исследование ИЛ-2 включает в себя понимание различий между этими механизмами связывания. В 2012 году Folding@home помогла открыть мутантную форму ИЛ-2, которая в триста раз эффективнее в своей роли в иммунной системе, но имеет меньше побочных эффектов. В экспериментах эта измененная форма значительно превзошла естественный ИЛ-2 в препятствовании росту опухолей. Фармацевтические компании проявили интерес к мутантной молекуле, и Национальные институты здравоохранения тестируют ее на большом количестве моделей опухолей, чтобы попытаться ускорить ее разработку в качестве терапевтического средства. [74] [75]
Несовершенный остеогенез , известный как болезнь хрупких костей, является неизлечимым генетическим заболеванием костей, которое может быть смертельным. Люди с этим заболеванием не способны производить функциональную соединительную костную ткань. Чаще всего это происходит из-за мутации коллагена типа I , [76] который выполняет множество структурных функций и является самым распространенным белком у млекопитающих . [77] Мутация вызывает деформацию тройной спирали коллагена , которая, если ее не разрушить естественным образом, приводит к аномальной и ослабленной костной ткани. [78] В 2005 году Folding@home протестировала новый квантово-механический метод, который улучшил предыдущие методы моделирования и который может быть полезен для будущих компьютерных исследований коллагена. [79] Хотя исследователи использовали Folding@home для изучения сворачивания и неправильного сворачивания коллагена, этот интерес представляет собой пилотный проект по сравнению с исследованиями болезни Альцгеймера и Хантингтона. [35]
Folding@home помогает в исследованиях, направленных на предотвращение распознавания и проникновения в биологические клетки некоторых вирусов , таких как грипп и ВИЧ . [35] В 2011 году Folding@home начал моделирование динамики фермента РНКазы H , ключевого компонента ВИЧ, чтобы попытаться разработать препараты для его дезактивации. [80] Folding@home также использовался для изучения слияния мембран , важного события для вирусной инфекции и широкого спектра биологических функций. Это слияние включает конформационные изменения вирусных белков слияния и стыковку белков , [36] но точные молекулярные механизмы, лежащие в основе слияния, остаются в значительной степени неизвестными. [81] События слияния могут состоять из более чем полумиллиона атомов, взаимодействующих в течение сотен микросекунд. Эта сложность ограничивает типичные компьютерные моделирования примерно десятью тысячами атомов за десятки наносекунд: разница в несколько порядков. [55] Разработка моделей для прогнозирования механизмов слияния мембран поможет в научном понимании того, как нацеливать этот процесс с помощью противовирусных препаратов. [82] В 2006 году ученые применили модели марковских состояний и сеть Folding@home, чтобы обнаружить два пути слияния и получить другие механистические знания. [55]
После детального моделирования от Folding@home небольших клеток, известных как везикулы , в 2007 году лаборатория Панде представила новый вычислительный метод для измерения топологии их структурных изменений во время слияния. [83] В 2009 году исследователи использовали Folding@home для изучения мутаций гемагглютинина гриппа , белка, который прикрепляет вирус к клетке- хозяину и способствует проникновению вируса. Мутации гемагглютинина влияют на то, насколько хорошо белок связывается с молекулами рецепторов клеточной поверхности хозяина , что определяет, насколько заразен штамм вируса для организма-хозяина. Знание эффектов мутаций гемагглютинина помогает в разработке противовирусных препаратов . [84] [85] По состоянию на 2012 год Folding@home продолжает моделировать сворачивание и взаимодействие гемагглютинина, дополняя экспериментальные исследования в Университете Вирджинии . [35] [86]
В марте 2020 года Folding@home запустила программу, призванную помочь исследователям по всему миру, которые работают над поиском лекарства и изучают больше о пандемии коронавируса . Первоначальная волна проектов имитирует потенциально лекарственно активируемые белковые мишени вируса SARS-CoV-2 и родственного вируса SARS-CoV, о котором имеется значительно больше данных. [87] [88] [89]
Лекарства функционируют, связываясь с определенными участками на целевых молекулах и вызывая некоторые желаемые изменения, такие как отключение цели или вызывая конформационные изменения . В идеале лекарство должно действовать очень специфично и связываться только со своей целью, не мешая другим биологическим функциям. Однако трудно точно определить, где и насколько плотно будут связываться две молекулы. Из-за ограничений вычислительной мощности текущие методы in silico обычно должны жертвовать скоростью ради точности ; например, использовать методы быстрой стыковки белков вместо вычислительно затратных расчетов свободной энергии . Вычислительная производительность Folding@home позволяет исследователям использовать оба метода и оценивать их эффективность и надежность. [39] [90] [91] Компьютерное проектирование лекарств может ускорить и снизить затраты на открытие лекарств. [38] В 2010 году Folding@home использовала MSM и расчеты свободной энергии для предсказания нативного состояния белка виллина с точностью до 1,8 ангстрема (Å) среднеквадратичного отклонения (RMSD) от кристаллической структуры , экспериментально определенной с помощью рентгеновской кристаллографии . Эта точность имеет значение для будущих методов предсказания структуры белка , в том числе для внутренне неструктурированных белков . [55] Ученые использовали Folding@home для исследования лекарственной устойчивости , изучая ванкомицин , антибиотик последнего средства , и бета-лактамазу , белок, который может расщеплять антибиотики, такие как пенициллин . [92] [93]
Химическая активность происходит вдоль активного сайта белка . Традиционные методы разработки лекарств включают в себя прочное связывание с этим сайтом и блокирование его активности, при условии, что целевой белок существует в одной жесткой структуре. Однако этот подход работает примерно только для 15% всех белков. Белки содержат аллостерические сайты , которые при связывании с малыми молекулами могут изменять конформацию белка и в конечном итоге влиять на активность белка. Эти сайты являются привлекательными мишенями для лекарств, но их обнаружение очень затратно с точки зрения вычислений . В 2012 году Folding@home и MSMs использовались для идентификации аллостерических сайтов в трех белках, имеющих медицинское значение: бета-лактамазе, интерлейкине-2 и РНКазе H. [ 93] [94]
Примерно половина всех известных антибиотиков вмешивается в работу рибосомы бактерий , большой и сложной биохимической машины, которая выполняет биосинтез белка путем трансляции информационной РНК в белки. Макролидные антибиотики закупоривают выходной туннель рибосомы, предотвращая синтез основных бактериальных белков. В 2007 году лаборатория Панде получила грант на изучение и разработку новых антибиотиков. [35] В 2008 году они использовали Folding@home для изучения внутренней части этого туннеля и того, как определенные молекулы могут на него влиять. [95] Полная структура рибосомы была определена только по состоянию на 2011 год, и Folding@home также моделировал рибосомальные белки , поскольку многие из их функций остаются в значительной степени неизвестными. [96]
Как и другие проекты распределенных вычислений , Folding@home — это онлайн- проект гражданской науки . В этих проектах неспециалисты вносят вычислительную мощность компьютера или помогают анализировать данные, полученные профессиональными учеными. Участники получают незначительное или не получают никакого очевидного вознаграждения.
Были проведены исследования мотивации гражданских ученых, и большинство из этих исследований показали, что участники мотивированы к участию из альтруистических соображений; то есть они хотят помочь ученым и внести вклад в развитие их исследований. [97] [98] [99] [100] Многие участники гражданской науки имеют скрытый интерес к теме исследования и тяготеют к проектам, которые находятся в интересующих их дисциплинах. Folding@home ничем не отличается в этом отношении. [101] Исследования, проведенные недавно с участием более 400 активных участников, показали, что они хотели помочь внести вклад в исследования, и что у многих были друзья или родственники, страдающие болезнями, которые изучают ученые Folding@home.
Folding@home привлекает участников, которые являются энтузиастами компьютерного оборудования. Эти группы привносят в проект значительный опыт и способны создавать компьютеры с передовой вычислительной мощностью. [102] [ нужна цитата для проверки ] Другие проекты распределенных вычислений привлекают таких участников, и проекты часто используются для оценки производительности модифицированных компьютеров, и этот аспект хобби учитывается благодаря соревновательному характеру проекта. Отдельные лица и команды могут соревноваться, чтобы увидеть, кто может обработать больше вычислительных блоков (ЦП).
Это последнее исследование Folding@home, включающее интервью и этнографическое наблюдение за онлайн-группами, показало, что команды энтузиастов оборудования иногда могут работать вместе, обмениваясь передовым опытом в отношении максимизации производительности обработки. Такие команды могут стать сообществами практики с общим языком и онлайн-культурой. Такая модель участия наблюдалась в других проектах распределенных вычислений. [103] [104]
Еще одно ключевое наблюдение относительно участников Folding@home заключается в том, что многие из них мужчины. [101] Это также наблюдалось в других распределенных проектах. Кроме того, многие участники работают в компьютерных и технологических рабочих местах и карьерах. [101] [105] [106]
Не все участники Folding@home являются энтузиастами оборудования. Многие участники запускают программное обеспечение проекта на немодифицированных машинах и принимают участие в конкурсе. К январю 2020 года количество пользователей сократилось до 30 000. [107] Однако трудно определить, какая доля участников является энтузиастами оборудования. Хотя, по словам руководителей проекта, вклад сообщества энтузиастов существенно больше с точки зрения вычислительной мощности. [108]

Производительность суперкомпьютера FLOPS оценивается с помощью устаревшего бенчмарка LINPACK . Это краткосрочное тестирование имеет трудности в точном отражении устойчивой производительности на реальных задачах, поскольку LINPACK более эффективно сопоставляется с аппаратным обеспечением суперкомпьютера. Вычислительные системы различаются по архитектуре и дизайну, поэтому прямое сравнение затруднено. Несмотря на это, FLOPS остаются основной метрикой скорости, используемой в суперкомпьютерах. [109] [ нужна цитата для проверки ] Напротив, Folding@home определяет свои FLOPS с помощью настенного времени , измеряя, сколько времени требуется его рабочим единицам для завершения. [110]
16 сентября 2007 года, во многом благодаря участию консолей PlayStation 3, проект Folding@home официально достиг устойчивого уровня производительности выше одного собственного петафлопса , став первой вычислительной системой любого типа, которая достигла этого. [111] [112] Самым быстрым суперкомпьютером Top500 на тот момент был BlueGene/L с производительностью 0,280 петафлопса. [113] В следующем году, 7 мая 2008 года, проект достиг устойчивого уровня производительности выше двух собственных петафлопсов, [114] за которым последовали три и четыре собственных петафлопса в августе 2008 года [115] [116] и 28 сентября 2008 года соответственно. [117] 18 февраля 2009 года Folding@home достиг пяти собственных петафлопс, [118] [119] и стал первым вычислительным проектом, который соответствовал этим пяти уровням. [120] [121] Для сравнения, самым быстрым суперкомпьютером ноября 2008 года был Roadrunner от IBM с производительностью 1,105 петафлопс. [122] 10 ноября 2011 года производительность Folding@home превысила шесть собственных петафлопс, что эквивалентно почти восьми x86 петафлопс. [112] [123] В середине мая 2013 года Folding@home достиг более семи собственных петафлопс, что эквивалентно 14,87 x86 петафлопс. Затем 21 июня он достиг восьми собственных петафлопс, а 9 сентября того же года — девяти, с 17,9 x86 петафлопс. [124] 11 мая 2016 года Folding@home объявила, что движется к достижению отметки 100 x86 петафлопс. [125]
Дальнейшее использование возросло благодаря повышению осведомленности и участия в проекте из-за пандемии коронавируса в 2020 году. 20 марта 2020 года Folding@home объявила в Twitter, что она работает с более чем 470 собственными петафлопсами, [126] что эквивалентно 958 x86 петафлопс. [127] К 25 марта она достигла 768 петафлопс, или 1,5 x86 эксафлопс, что сделало ее первой вычислительной системой exaFLOP . [128]
По состоянию на 20 июля 2024 года [update]вычислительная мощность Folding@home составляет 13,8 петафлопс или 26,9 x86 петафлопс. [129]
Подобно другим распределенным вычислительным проектам, Folding@home количественно оценивает вычислительный вклад пользователя в проект с помощью системы баллов. [130] Все единицы из данного белкового проекта имеют единый базовый балл, который определяется путем сравнения одной или нескольких рабочих единиц из этого проекта на официальной эталонной машине до того, как проект будет выпущен. [130] Каждый пользователь получает эти базовые баллы за выполнение каждой рабочей единицы, хотя с помощью ключа доступа он может получить дополнительные бонусные баллы за надежное и быстрое выполнение единиц, которые требуют больших вычислительных затрат или имеют больший научный приоритет. [131] [132] Пользователи также могут получать баллы за свою работу от клиентов на нескольких машинах. [133] Эта система баллов пытается сопоставить присужденные баллы с ценностью научных результатов. [130]
Пользователи могут регистрировать свои вклады в команду, которая объединяет баллы всех своих участников. Пользователь может создать свою собственную команду или присоединиться к существующей команде. В некоторых случаях команда может иметь собственные источники помощи или набора, управляемые сообществом, такие как интернет-форум . [134] Баллы могут способствовать дружескому соревнованию между отдельными лицами и командами, чтобы вычислить максимальную сумму для проекта, что может принести пользу сообществу фолдинга и ускорить научные исследования. [130] [135] [136] Индивидуальная и командная статистика публикуется на веб-сайте Folding@home. [130]
Если пользователь не формирует новую команду или не присоединяется к существующей команде, этот пользователь автоматически становится частью команды "Default". Эта команда "Default" имеет номер команды "0". Статистика накапливается как для этой команды "Default", так и для специально названных команд.
Программное обеспечение Folding@home на стороне пользователя состоит из трех основных компонентов: рабочих модулей, ядер и клиента.
Рабочая единица — это данные о белке, которые клиенту предлагается обработать. Рабочие единицы — это часть моделирования между состояниями в марковской модели . После того, как рабочая единица загружена и полностью обработана компьютером добровольца, она возвращается на серверы Folding@home, которые затем начисляют добровольцу кредитные баллы. Этот цикл повторяется автоматически. [135] Все рабочие единицы имеют связанные с ними крайние сроки, и если этот крайний срок превышен, пользователь может не получить кредит, а единица будет автоматически перевыдана другому участнику. Поскольку сворачивание белка происходит последовательно, и многие рабочие единицы генерируются из своих предшественников, это позволяет общему процессу моделирования продолжаться нормально, если рабочая единица не возвращается по истечении разумного периода времени. Из-за этих крайних сроков минимальным системным требованием для Folding@home является процессор Pentium 3 450 МГц с потоковыми расширениями SIMD (SSE). [133] Однако рабочие блоки для высокопроизводительных клиентов имеют гораздо более короткие сроки, чем для однопроцессорного клиента, поскольку большая часть научных преимуществ зависит от быстрого завершения моделирования. [137]
Перед публичным выпуском рабочие единицы проходят несколько этапов контроля качества , чтобы не допустить полной доступности проблемных единиц. Эти этапы тестирования включают внутреннее, бета-тестирование и расширенное тестирование перед окончательным полным выпуском в Folding@home. [138] Рабочие единицы Folding@home обычно обрабатываются только один раз, за исключением редких случаев возникновения ошибок во время обработки. Если это происходит для трех разных пользователей, единица автоматически изымается из распространения. [139] [140] Форум поддержки Folding@home можно использовать для различения проблем, возникающих из-за проблемного оборудования, и плохих рабочих единиц. [141]
Специализированные программы молекулярной динамики, называемые «FahCores» и часто сокращенно «ядра», выполняют вычисления на рабочей единице в качестве фонового процесса . Значительное большинство ядер Folding@home основаны на GROMACS , [135] одном из самых быстрых и популярных пакетов программного обеспечения молекулярной динамики, который в основном состоит из вручную оптимизированного кода на языке ассемблера и аппаратных оптимизаций. [142] [143] Хотя GROMACS является программным обеспечением с открытым исходным кодом и между лабораторией Pande и разработчиками GROMACS ведутся совместные усилия, Folding@home использует лицензию с закрытым исходным кодом , чтобы гарантировать достоверность данных. [144] Менее активные ядра включают ProtoMol и SHARPEN. Folding@home использовала AMBER , CPMD , Desmond и TINKER , но с тех пор они были сняты с производства и больше не используются. [4] [145] [146] Некоторые из этих ядер выполняют явные расчеты сольватации, в которых окружающий растворитель (обычно вода) моделируется атом за атомом; в то время как другие выполняют неявные методы сольватации, где растворитель рассматривается как математический континуум. [147] [148] Ядро отделено от клиента, чтобы научные методы могли обновляться автоматически, не требуя обновления клиента. Ядра периодически создают контрольные точки расчетов , так что если они будут прерваны, они смогут возобновить работу с этой точки при запуске. [135]

Участник Folding@home устанавливает клиентскую программу на свой персональный компьютер . Пользователь взаимодействует с клиентом, который управляет другими компонентами программного обеспечения в фоновом режиме. Через клиент пользователь может приостановить процесс складывания, открыть журнал событий, проверить ход выполнения работы или просмотреть личную статистику. [149] Клиенты-компьютеры непрерывно работают в фоновом режиме с очень низким приоритетом, используя простаивающую вычислительную мощность, так что обычное использование компьютера не влияет на него. [133] Максимальное использование ЦП можно настроить с помощью настроек клиента. [149] [150] Клиент подключается к серверу Folding@home и извлекает рабочую единицу, а также может загрузить соответствующее ядро для настроек клиента, операционной системы и базовой аппаратной архитектуры. После обработки рабочая единица возвращается на серверы Folding@home. Клиенты-компьютеры адаптированы для однопроцессорных и многоядерных процессорных систем, а также графических процессоров . Разнообразие и мощность каждой аппаратной архитектуры дает Folding@home возможность эффективно завершать многие типы симуляций в установленные сроки (за несколько недель или месяцев, а не лет), что имеет значительную научную ценность. Вместе эти клиенты позволяют исследователям изучать биомедицинские вопросы, которые ранее считались непрактичными для решения с помощью вычислений. [39] [135] [137]
Профессиональные разработчики программного обеспечения отвечают за большую часть кода Folding@home, как для клиентской, так и для серверной части. В команду разработчиков входят программисты из Nvidia , ATI , Sony и Cauldron Development. [151] Клиенты могут быть загружены только с официального сайта Folding@home или его коммерческих партнеров, и будут взаимодействовать только с компьютерными файлами Folding@home. Они будут загружать и скачивать данные с серверов данных Folding@home (через порт 8080, с 80 в качестве альтернативы), а связь проверяется с помощью 2048-битных цифровых подписей . [133] [152] Хотя графический пользовательский интерфейс клиента (GUI) имеет открытый исходный код, [153] клиент является проприетарным программным обеспечением, ссылаясь на безопасность и научную целостность в качестве причин. [154] [155] [156]
Однако это обоснование использования проприетарного программного обеспечения оспаривается, поскольку, хотя лицензия может быть принудительно применена в юридической сфере ретроспективно, она практически не предотвращает модификацию (также известную как исправление ) исполняемых двоичных файлов . Аналогичным образом, распространение только двоичных файлов не предотвращает вредоносную модификацию исполняемого двоичного кода, либо посредством атаки «человек посередине» во время загрузки через Интернет, [157] либо путем перераспределения двоичных файлов третьей стороной, которые были ранее изменены либо в их двоичном состоянии (т. е. исправлены ), [158] или путем декомпиляции [159] и повторной компиляции их после изменения. [160] [161] Эти изменения возможны, если двоичные файлы — и транспортный канал — не подписаны , а получатель/система не может проверить цифровую подпись, в этом случае необоснованные изменения должны быть обнаружены, но не всегда. [162] В любом случае, поскольку в случае Folding@home входные данные и выходные результаты, обработанные клиентским программным обеспечением, имеют цифровую подпись, [133] [152] целостность работы может быть проверена независимо от целостности самого клиентского программного обеспечения.
Folding@home использует библиотеки программного обеспечения Cosm для работы в сети. [135] [151] Folding@home был запущен 1 октября 2000 года и был первым проектом распределенных вычислений, нацеленным на биомолекулярные системы. [163] Его первым клиентом была заставка , которая работала, пока компьютер не использовался. [164] [165] В 2004 году лаборатория Панде сотрудничала с Дэвидом П. Андерсоном для тестирования дополнительного клиента на основе фреймворка BOINC с открытым исходным кодом . Этот клиент был выпущен в закрытую бета-версию в апреле 2005 года; [166] однако метод стал неработоспособным и был отложен в июне 2006 года. [167]
Специализированное оборудование графических процессоров (GPU) предназначено для ускорения рендеринга трехмерных графических приложений, таких как видеоигры, и может значительно превосходить CPU для некоторых типов вычислений. GPU являются одной из самых мощных и быстрорастущих вычислительных платформ, и многие ученые и исследователи занимаются вычислениями общего назначения на графических процессорах (GPGPU). Однако оборудование GPU трудно использовать для неграфических задач и обычно требует значительной реструктуризации алгоритмов и углубленного понимания базовой архитектуры. [168] Такая настройка является сложной задачей, особенно для исследователей с ограниченными ресурсами разработки программного обеспечения. Folding@home использует библиотеку OpenMM с открытым исходным кодом , которая использует шаблон проектирования моста с двумя уровнями интерфейса прикладного программирования (API) для сопряжения программного обеспечения молекулярного моделирования с базовой аппаратной архитектурой. С добавлением аппаратных оптимизаций моделирование GPU на основе OpenMM не требует значительных модификаций, но достигает производительности, почти равной настроенному вручную коду GPU, и значительно превосходит реализации CPU. [147] [169]
До 2010 года вычислительная надежность оборудования потребительского класса GPGPU была в значительной степени неизвестна, и косвенные доказательства, связанные с отсутствием встроенного обнаружения и исправления ошибок в памяти GPU, вызывали опасения по поводу надежности. В первом крупномасштабном тесте научной точности GPU исследование 2010 года более 20 000 хостов в сети Folding@home обнаружило программные ошибки в подсистемах памяти двух третей протестированных GPU. Эти ошибки тесно связаны с архитектурой платы, хотя исследование пришло к выводу, что надежные вычисления GPU вполне возможны, если уделять внимание характеристикам оборудования, таким как обнаружение ошибок на стороне программного обеспечения. [170]
Первое поколение GPU-клиента Folding@home (GPU1) было выпущено для публики 2 октября 2006 года [167] , обеспечив ускорение некоторых вычислений в 20–30 раз по сравнению с аналогами GROMACS на базе CPU . [171] Это был первый случай использования GPU для распределенных вычислений или крупных расчетов молекулярной динамики. [172] [173] GPU1 дал исследователям значительные знания и опыт в разработке программного обеспечения GPGPU , но в ответ на научные неточности с DirectX 10 апреля 2008 года на смену ему пришло GPU2, второе поколение клиента. [171] [174] После введения GPU2, GPU1 был официально снят с производства 6 июня. [171] По сравнению с GPU1, GPU2 был более надежным и производительным с научной точки зрения, работал на графических процессорах Nvidia с поддержкой ATI и CUDA и поддерживал более продвинутые алгоритмы, более крупные белки и визуализацию моделирования белков в реальном времени. [175] [176] После этого, 25 мая 2010 года, было выпущено третье поколение клиента GPU Folding@home (GPU3). Несмотря на обратную совместимость с GPU2, GPU3 был более стабильным, эффективным и гибким в своих научных возможностях, [177] и использовал OpenMM поверх фреймворка OpenCL . [177] [178] Хотя эти клиенты GPU3 изначально не поддерживали операционные системы Linux и macOS , пользователи Linux с видеокартами Nvidia могли запускать их через программное приложение Wine . [179] [180] Графические процессоры остаются самой мощной платформой Folding@home в FLOPS . По состоянию на ноябрь 2012 года клиенты GPU составляют 87% от всей пропускной способности x86 FLOPS проекта. [181]
Встроенная поддержка видеокарт Nvidia и AMD под управлением Linux была представлена в FahCore 17, который использует OpenCL вместо CUDA. [182]

С марта 2007 года по ноябрь 2012 года Folding@home использовала вычислительную мощность PlayStation 3s . На момент своего создания ее основной потоковый процессор Cell обеспечивал 20-кратное увеличение скорости по сравнению с ПК для некоторых вычислений, вычислительная мощность, которую нельзя было найти в других системах, таких как Xbox 360. [39] [183] Высокая скорость и эффективность PS3 представили другие возможности для стоящих оптимизаций в соответствии с законом Амдаля и значительно изменили компромисс между вычислительной эффективностью и общей точностью, что позволило использовать более сложные молекулярные модели при небольших дополнительных вычислительных затратах. [184] Это позволило Folding@home выполнять биомедицинские расчеты, которые в противном случае были бы невыполнимы с вычислительной точки зрения. [185]
Клиент PS3 был разработан в результате совместных усилий Sony и лаборатории Pande и впервые был выпущен как автономный клиент 23 марта 2007 года. [39] [186] Его выпуск сделал Folding@home первым проектом распределенных вычислений, использующим PS3. [187] 18 сентября следующего года клиент PS3 стал каналом Life with PlayStation с момента его запуска. [188] [189] По типам вычислений, которые он мог выполнять, на момент своего появления клиент находился между гибкостью центрального процессора и скоростью графического процессора. [135] Однако, в отличие от клиентов, работающих на персональных компьютерах , пользователи не могли выполнять другие действия на своих PS3 во время работы Folding@home. [185] Единая консольная среда PS3 упростила техническую поддержку и сделала Folding@home более удобным для пользователя . [39] PS3 также имела возможность быстро передавать данные на свой графический процессор, который использовался для визуализации текущей динамики белка в режиме реального времени на атомном уровне. [184]
6 ноября 2012 года Sony прекратила поддержку клиента Folding@home PS3 и других сервисов, доступных в рамках Life with PlayStation. За пять лет и семь месяцев существования более 15 миллионов пользователей внесли более 100 миллионов часов вычислений в Folding@home, что значительно помогло проекту в исследовании болезней. После обсуждений с лабораторией Pande, Sony решила прекратить приложение. Pande посчитала клиент PlayStation 3 «переломным моментом» для проекта. [190] [191] [192]
Folding@home может использовать возможности параллельных вычислений современных многоядерных процессоров. Возможность использовать несколько ядер ЦП одновременно позволяет завершить полную симуляцию намного быстрее. Работая вместе, эти ядра ЦП завершают отдельные рабочие единицы пропорционально быстрее, чем стандартный однопроцессорный клиент. Этот метод имеет научную ценность, поскольку он позволяет выполнять гораздо более длинные траектории симуляции за то же время и снижает традиционные трудности масштабирования большой симуляции на множество отдельных процессоров. [193] Публикация 2007 года в журнале Journal of Molecular Biology опиралась на многоядерную обработку для моделирования сворачивания части белка виллина примерно в 10 раз дольше, чем это было возможно с однопроцессорным клиентом, в соответствии с экспериментальными скоростями сворачивания. [194]
В ноябре 2006 года клиенты симметричной многопроцессорной обработки (SMP) первого поколения были публично выпущены для открытого бета-тестирования, называемого SMP1. [167] Эти клиенты использовали протоколы связи Message Passing Interface (MPI) для параллельной обработки, так как в то время ядра GROMACS не были предназначены для использования с несколькими потоками. [137] Это был первый случай, когда проект распределенных вычислений использовал MPI. [195] Хотя клиенты хорошо работали в операционных системах на базе Unix , таких как Linux и macOS, они были проблемными под Windows . [193] [195] 24 января 2010 года SMP2, второе поколение клиентов SMP и преемник SMP1, был выпущен в качестве открытой бета-версии и заменил сложный MPI более надежной реализацией на основе потоков . [132] [151]
SMP2 поддерживает испытание специальной категории рабочих единиц bigadv , разработанных для моделирования белков, которые являются необычно большими и вычислительно интенсивными и имеют большой научный приоритет. Первоначально эти единицы требовали минимум восьми ядер ЦП, [196] что было увеличено до шестнадцати позже, 7 февраля 2012 года. [197] Наряду с этими дополнительными требованиями к оборудованию по сравнению со стандартными рабочими единицами SMP2, они требуют больше системных ресурсов, таких как оперативная память (ОЗУ) и пропускная способность Интернета . Взамен пользователи, которые их запускают, вознаграждаются 20%-ным увеличением по сравнению с бонусной системой баллов SMP2. [198] Категория bigadv позволяет Folding@home запускать особенно требовательные симуляции в течение длительного времени, которые ранее требовали использования суперкомпьютерных кластеров и не могли быть выполнены где-либо еще на Folding@home. [196] Многие пользователи с оборудованием, способным запускать модули bigadv, позже лишились своей аппаратной настройки, которая считалась неподходящей для рабочих модулей bigadv, когда были увеличены минимальные требования к ядрам ЦП, в результате чего они могли запускать только обычные рабочие модули SMP. Это разочаровало многих пользователей, которые вложили значительные суммы денег в программу, но вскоре после этого их оборудование стало устаревшим для целей bigadv. В результате в январе 2014 года Панде объявил, что программа bigadv завершится 31 января 2015 года. [199]

Клиент V7 — это седьмое и последнее поколение клиентского программного обеспечения Folding@home, полностью переписанное и объединенное с предыдущими клиентами для операционных систем Windows , macOS и Linux . [200] [201] Он был выпущен 22 марта 2012 года. [202] Как и его предшественники, V7 может запускать Folding@home в фоновом режиме с очень низким приоритетом , позволяя другим приложениям использовать ресурсы ЦП по мере необходимости. Он разработан, чтобы сделать установку, запуск и эксплуатацию более удобными для новичков и предложить исследователям большую научную гибкость, чем предыдущие клиенты. [203] V7 использует Trac для управления своими тикетами ошибок , чтобы пользователи могли видеть процесс разработки и предоставлять обратную связь. [201]
V7 состоит из четырех интегрированных элементов. Пользователь обычно взаимодействует с открытым исходным кодом графического интерфейса V7 , называемого FAHControl. [153] [204] Он имеет режимы пользовательского интерфейса Novice, Advanced и Expert и имеет возможность контролировать, настраивать и управлять многими удаленными клиентами фолдинга с одного компьютера. FAHControl управляет FAHClient, внутренним приложением, которое, в свою очередь, управляет каждым FAHSlot (или слотом ). Каждый слот действует как замена ранее отдельных однопроцессорных, SMP или GPU-клиентов Folding@home v6, поскольку он может загружать, обрабатывать и выгружать рабочие единицы независимо. Функция FAHViewer, смоделированная по образцу средства просмотра PS3, отображает трехмерную визуализацию в реальном времени, если она доступна, белка, который в данный момент обрабатывается. [200] [201]
В 2014 году был выпущен клиент для веб-браузеров Google Chrome и Chromium , позволяющий пользователям запускать Folding@home в своем веб-браузере. Клиент использовал функцию Google Native Client (NaCl) в веб-браузерах на базе Chromium для запуска кода Folding@home на скорости, близкой к родной, в песочнице на компьютере пользователя. [205] Из-за постепенного отказа от NaCL и изменений в Folding@home веб-клиент был окончательно закрыт в июне 2019 года. [206]
В июле 2015 года в Google Play был выпущен клиент для мобильных телефонов Android для устройств под управлением Android 4.4 KitKat или более поздней версии. [207] [208]
16 февраля 2018 года клиент Android, который был предложен в сотрудничестве с Sony , был удален из Google Play. Было объявлено о планах предложить альтернативу с открытым исходным кодом в будущем. [209]
Rosetta@home — это проект распределенных вычислений, нацеленный на прогнозирование структуры белка, и один из самых точных предсказателей третичной структуры . [210] [211] Конформационные состояния из программного обеспечения Rosetta могут быть использованы для инициализации модели марковских состояний в качестве отправных точек для моделирования Folding@home. [25] И наоборот, алгоритмы прогнозирования структуры могут быть улучшены с помощью термодинамических и кинетических моделей и аспектов выборки моделирования сворачивания белка. [212] Поскольку Rosetta пытается предсказать только конечное свернутое состояние, а не то, как происходит сворачивание, Rosetta@home и Folding@home являются взаимодополняющими и решают совершенно разные молекулярные вопросы. [25] [213]
Anton — это специализированный суперкомпьютер, созданный для моделирования молекулярной динамики. В октябре 2011 года Anton и Folding@home были двумя самыми мощными системами молекулярной динамики. [214] Anton уникален своей способностью создавать отдельные сверхдлинные, требующие больших вычислительных затрат молекулярные траектории, [215] например, одну в 2010 году, которая достигла миллисекундного диапазона. [216] [217] Эти длинные траектории могут быть особенно полезны для некоторых типов биохимических проблем. [218] [219] Однако Anton не использует модели марковских состояний (MSM) для анализа. В 2011 году лаборатория Панде построила MSM из двух 100- мкс симуляций Anton и обнаружила альтернативные пути сворачивания, которые не были видны в традиционном анализе Anton. Они пришли к выводу, что между MSM, построенными из ограниченного числа длинных траекторий, и одной, собранной из многих более коротких траекторий, мало различий. [215] В июне 2011 года Folding@home добавил выборку симуляции Anton, чтобы лучше определить, как его методы сравниваются с методами Anton. [220] [221] Однако, в отличие от более коротких траекторий Folding@home, которые более поддаются распределенным вычислениям и другим методам распараллеливания, более длинные траектории не требуют адаптивной выборки для достаточной выборки фазового пространства белка . В связи с этим возможно, что комбинация методов симуляции Anton и Folding@home обеспечит более тщательную выборку этого пространства. [215]
{{cite journal}}: CS1 maint: multiple names: authors list (link){{cite journal}}: CS1 maint: DOI inactive as of June 2024 (link) CS1 maint: bot: original URL status unknown (link){{cite journal}}: CS1 maint: multiple names: authors list (link){{cite news}}: CS1 maint: numeric names: authors list (link) Насколько нам известно, это первые рецензируемые результаты проекта распределенных вычислений, связанного с раком.{{cite book}}: CS1 maint: location missing publisher (link){{citation}}: CS1 maint: numeric names: authors list (link)